Random-Centroid Optimization (RCO) Method to Improve the Adhesion of Biocontrol Lactic Acid Bacteria (LAB) Lac 9-3 and Its Effect on the Microflora Structure of Refrigerated Litopenaeus vannamei
-
摘要: 生防乳酸菌粘附是其在食品表面定植并发挥作用的第一步。为进一步提升乳酸菌Lac 9-3在凡纳滨对虾表面的粘附性,探究其对冷藏凡纳滨对虾腐败菌生长的影响,本研究采用随机质心映射优化法(Random-Centroid Optimization,RCO)优化了乳酸菌Lac 9-3的接种条件(包括接种液浓度、接种菌株生长阶段、浸泡时间与接种液pH)。同时,运用高通量测序技术,分析经乳酸菌Lac 9-3处理后的凡纳滨对虾在冷藏第0、8和14 d菌群多样性与组成的差异,探究乳酸菌Lac 9-3对冷藏凡纳滨对虾菌群结构的影响。结果表明,乳酸菌Lac 9-3的最佳接种条件为:接种液浓度为108 CFU/mL、菌株生长阶段为14.1 h(对应稳定期初期),浸泡时间为17.41 min,接种液pH为6.51。在最佳接种条件下,乳酸菌Lac 9-3在凡纳滨对虾表面的粘附数量达到2.08×109 CFU/g,较同浓度对照组增加72.65%。此外,菌相结果显示,乳酸菌Lac 9-3可通过抑制凡纳滨对虾表面优势腐败菌希瓦氏菌属(Shewanella)、肉食杆菌属(Carnobacterium)、别弧菌属(Aliivibrio)与弧菌属(Vibrio)的生长繁殖,调节冷藏期间凡纳滨对虾的菌群结构。乳酸菌Lac 9-3粘附性的提升增加了其在凡纳滨对虾表面的粘附数量,从而调控冷藏过程中凡纳滨对虾的菌群结构并影响其腐败进程,揭示了乳酸菌Lac 9-3在水产品保鲜中的应用潜力。Abstract: The adhesion on the food surface of lactic acid bacteria (LAB) plays an important role in their colonization and biological control. The inoculated conditions of LAB Lac 9-3 (including the inoculum concentration, bacterial growth stage, soaking time, and inoculum pH) were optimized using the random-centroid optimization (RCO) method. Meanwhile, the effect of LAB Lac 9-3 on the growth and microflora of spoilage bacteria of Litopenaeus vannamei was also investigated using the high throughput sequencing technology during the storage time at 0, 8, and 14 days. The results indicated that the optimal inoculated conditions of LAB Lac 9-3 were as follows: The inoculum concentration was 108 CFU/mL, the growth stage was 14.1 h (corresponding to the early stabilization period), the soaking time was 17.41 min, and the inoculum pH was 6.51. The adhesion quantity of LAB Lac 9-3 reached 2.08×109 CFU/g under the optimal inoculated conditions, which obtained a 72.65% increase compared to that of the control group at the same concentration. Besides, the growth of Shewanella, Carnobacterium, Aliivibrio, and Vibrio in L. vannamei treated by LAB Lac 9-3 was significantly inhibited, indicating that improving the adhesion of LAB Lac 9-3 could increase the adhesion quantity on the surface of L. vannamei. The LAB Lac 9-3 might process the application potential in food preservation due to its regulating role in microflora and the spoilage process of aquatic products.
-
水产品营养价值丰富,在贮藏流通中极易腐败变质[1],因此,开发有效的加工处理方法以延长水产品的保质期十分必要[2-3]。生物保鲜是满足食品安全标准且不对食品的感官质量产生负面影响的一种新兴保鲜技术,乳酸菌保鲜作为一种典型的生物保鲜技术已被研究用于水产品保鲜中[4-5]。但是,乳酸菌在水产品保鲜中的作用效果不稳定,其难点在于乳酸菌在水产品表面的粘附性较低[6]。乳酸菌粘附是其定植并产生作用的第一步[7-8],并影响乳酸菌的抑菌作用、信息交流等[9]。Said等[10]提出乳酸菌主要通过替代或排斥作用、竞争营养物质等发挥其抗菌活性,这都与乳酸菌的粘附性紧密相关。此外,乳酸菌在食品表面的粘附性可有效改变食品表面的理化性质及食用品质[11]。
目前,已有大量研究证实接种液浓度、接种菌株生长阶段、浸泡时间、接种液pH等接种条件是影响乳酸菌粘附作用的重要因素[12]。因此,可通过优化以上接种条件来提升乳酸菌的粘附性。随机质心映射优化法(Random-Centroid Optimization,RCO)是一种灵活且具有全局性的优化程序,可根据实际条件及现实因素灵活调整因素范围,并已成功应用于优化定点诱变、食品产品的优化和工艺开发等[13]。与常用的正交设计法和响应面优化法相比,RCO法可大量减少试验次数,节约试验成本[14]。
凡纳滨对虾(Litopenaeus vannamei)是世界养殖范围最广的商业虾种之一,也是一种具有经济代表性的水产食品[15]。乳酸菌通过在凡纳滨对虾表面大量粘附,优先占据粘附位点并形成种群优势,从而抑制腐败菌的生长繁殖,是其能够发挥显著抗菌作用的关键途径。因此,乳酸菌诱导的菌群结构变化对其保鲜作用探究具有重要意义。乳酸菌Lac 9-3是从冷水鱼肠道中分离筛选出的高粘附性乳酸菌,可显著抑制水产品腐败菌(希瓦氏菌Shewanella、不动杆菌Acinetobacter、嗜水气单胞菌Aeromonas和假单胞菌Pseudomonas)的生长,有望应用于水产品保鲜。为进一步提升乳酸菌Lac 9-3的生防作用效果,本研究采用RCO法,通过调节接种液浓度、接种菌株体生长阶段、浸泡时间与接种液pH四个接种条件优化乳酸菌Lac 9-3在凡纳滨对虾表面的粘附性,并验证优化效果。同时,探究乳酸菌Lac 9-3对冷藏凡纳滨对虾菌群结构的影响,为生防乳酸菌Lac 9-3应用于水产品保鲜提供理论依据。
1. 材料与方法
1.1 材料与仪器
乳酸菌菌株Lac 9-3 中国海洋大学水产品高值化利用实验室保存,经过生理生化分析和16S rDNA鉴定为植物乳杆菌(Lactiplantibacillus plantarum);鲜活凡纳滨对虾(L. vannamei) 购于当地水产市场,大小、体形、体色均一且正常,平均重量为20±1 g,30 min内保活运输至实验室;氯化钠、氢氧化钠、盐酸等化学试剂 分析纯,国药集团化学试剂有限公司;MRS琼脂培养基、MRS肉汤培养基 青岛海博生物技术有限公司,121 ℃灭菌20 min备用;FastDNA® Spin Kit for Soil 美国MP Biomedicals公司;AxyPrep DNA Gel Extraction Kit 美国Axygen Biosciences公司。
YXQ-75SII高压灭菌锅 上海博迅医疗生物仪器股份有限公司;SJ-CJ-2FDQ超净工作台 苏洁医疗器械(苏州)有限公司;TGL-16M离心机 湖南湘仪实验室仪器开发公司;超微量分光光度计NanoDrop 2000 美国Thermo Fisher Scientific公司;ABI GeneAmp® 9700型PCR仪 美国ABI公司;Illumina Miseq测序仪 美国Illumina公司;Quantus™ Fluorometer 美国Promega公司。
1.2 实验方法
1.2.1 菌株培养
将乳酸菌Lac 9-3以三区画线的方式在MRS琼脂上活化,37 ℃静置培养24 h。活化两次后挑取生长良好且细胞形态完整的单菌落,接种于MRS肉汤中,37 ℃静置培养24 h。随后以1%(v/v)的接种量进行第二次活化,培养至对数期使用。
1.2.2 对虾样品前处理
鲜活凡纳滨对虾经-20 ℃无菌冰无痛猝死,去头、去壳、去虾线,备用。上述样品依次经无菌水冲洗、75%酒精浸泡3 min、无菌风干燥同时紫外线照射60 min以获得无菌对虾样品[16]。
1.2.3 接菌实验
通过控制乳酸菌Lac 9-3的培养时间(6~24 h)制备不同生长阶段的悬浮液,使用无菌生理盐水调节悬浮液浓度分别为103、104、105、106、107、108 CFU/mL,调节悬浮液pH为设定值(3~8)。随机称取相同质量的无菌对虾样品,分别置于100 mL上述制备的悬浮液中浸泡一定时间(5~30 min)后取出,立即置于4 ℃冰箱中冷藏24 h。
1.2.4 乳酸菌粘附数量测定
乳酸菌粘附数量测定参照Faten等[11]的方法并适当修改。从4 ℃冰箱中取出制备的对虾样品,置于无菌生理盐水中剧烈振荡5 min获得菌悬液,采用菌落计数法在MRS琼脂平板中计算乳酸菌单菌落数量,并设置空白对照(无菌生理盐水代替乳酸菌Lac 9-3悬浮液)。
1.2.5 随机质心映射优化
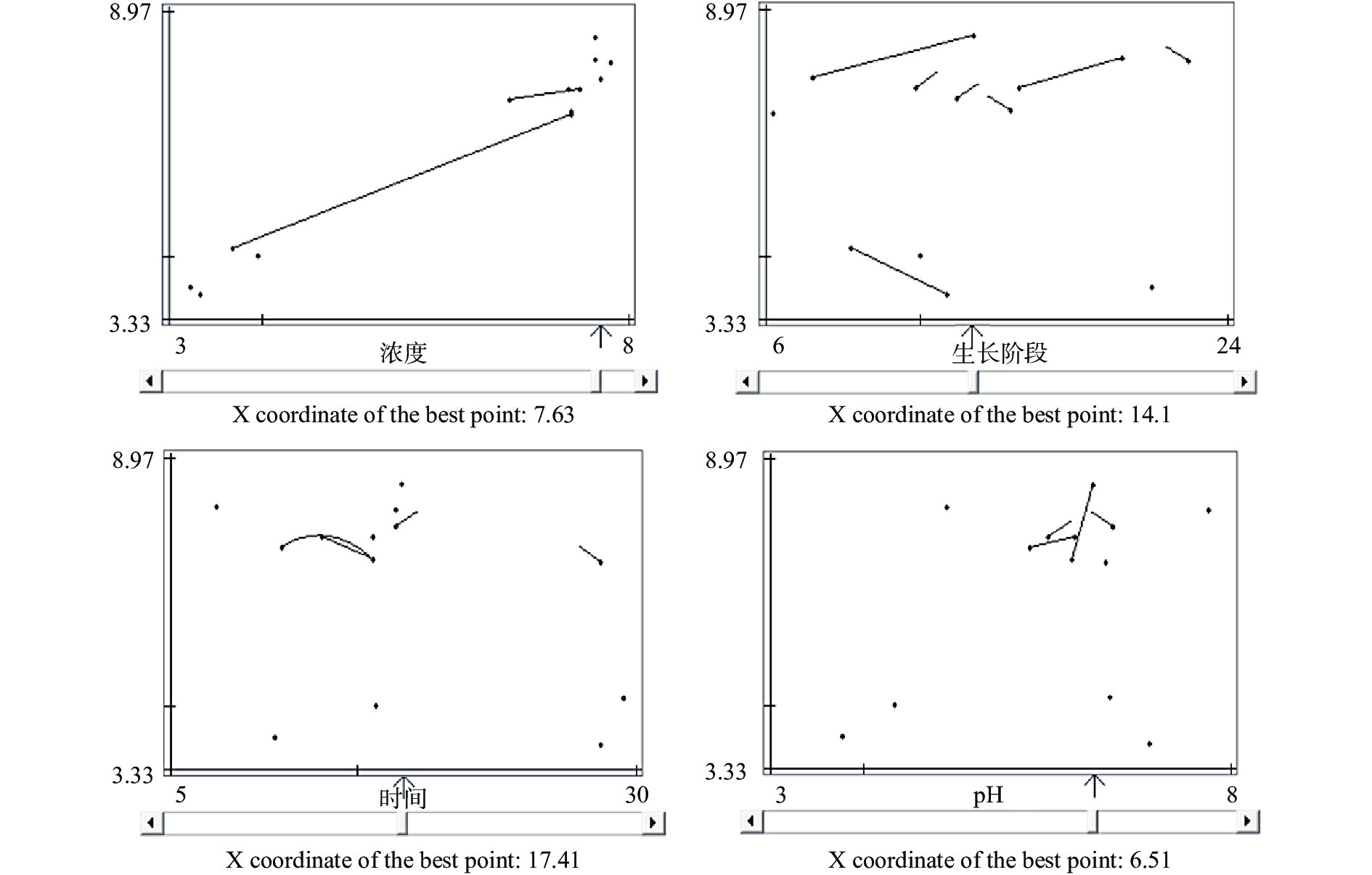
RCO程序参照Nakai等[17]的方法进行。根据任大勇[18]、王嘉悦[19]报道的影响乳酸菌粘附性的主要因素及其范围,并结合冷藏凡纳滨对虾保鲜的实际应用条件,确定以下接种条件及其范围:接种液浓度(103~108 CFU/mL),接种菌株生长阶段(6~24 h),浸泡时间(5~30 min),接种液pH(3~8)。将每个因素的最大值和最小值依次输入RCO程序进行随机搜索试验设计,根据各因素设置的因子值完成随机试验。归一化后的结果被输入RCO程序作为响应,质心搜索被用来缩小四个因素最合适的组合范围。对每个提取目标值提出了四组新的因子值,完成质心试验后再次将归一化后的结果输入RCO程序。最后,以映射的形式得到最佳因子值集,根据映射优化图中映射结果的分散程度判断是否需要进行下一轮循环[13]。
1.2.6 验证实验
为了验证RCO优化对乳酸菌Lac 9-3在凡纳滨对虾表面粘附性的提升效果,共设置以下3个分组:RCO优化组(使用RCO优化得到的最佳因子值)、空白对照组(正常接种条件)和同浓度对照组(接种液浓度与RCO优化组相同,其他条件与正常接种条件一致),对虾处理、接菌实验与乳酸菌粘附数量测定同1.2.3、1.2.4和1.2.5。
1.2.7 虾体表面微生物提取
将处理后的凡纳滨对虾随机称重分组,分别于乳酸菌Lac 9-3接种液(基于RCO优化后的接种条件)、无菌生理盐水(对照组)中浸泡后立即取出,放入无菌拉链袋中置于4 ℃冰箱中冷藏14 d至完全腐败。分别在冷藏第0、8、14 d随机取样,称取20 g虾样剪断后与80 mL无菌生理盐水在恒温振荡器中充分混匀30 min,以将虾体表面微生物提取到无菌生理盐水中。取上清液在4 ℃、10000 r/min条件下离心10 min,重复离心三次得菌体沉淀。
1.2.8 DNA抽提和PCR扩增
参照李冉等[20]的方法并作适当修改,使用FastDNA® Spin Kit for Soil并依据其说明书抽提样本中的微生物群落总DNA。338F(5'-ACTCCTACGGGAGGCAGCAG-3')和806R(5'-GGACTACHVGGGTWTCTAAT-3')分别用于16S rRNA基因V3~V4可变区的PCR扩增,具体扩增步骤如下:95 ℃预变性3 min,经过27次循环(95 ℃变性30 s,55 ℃退火30 s,72 ℃延伸30 s)后,72 ℃稳定延伸10 min,最后置于4 ℃条件下保存。每个样本三个重复。
1.2.9 Illumina Miseq测序与数据处理
基于Illumina公司的Miseq PE 300平台,高通量测序由上海美吉生物医药科技有限公司完成。使用Fastp软件对原始测序序列进行质控[21],使用Uparse软件(version 11),根据97%的相似度对序列进行OTU聚类并剔除嵌合体[22-23]。使用Qiime软件(version 1.9.1)进行物种多样性分析[24],利用RDP Classifier(version 2.13)对每条序列进行物种分类注释[25],比对SILVA 16S rRNA数据库,设置比对阈值为70%。
1.3 数据处理
所有试验重复三次,结果表示为平均值±标准差,使用Origin 2021(OriginLab,USA)软件绘制统计图,使用SPSS 26.0软件(SPSS Inc.,Chicago,IL,USA)进行显著性分析、方差比较等,P<0.05表示具有显著性差异。
2. 结果与分析
2.1 随机搜索试验
确定随机搜索试验条件及其范围是进行RCO的第一步。研究指出接种液浓度、接种菌株生长阶段、浸泡时间、接种液pH等外界条件是影响乳酸菌在介质表面粘附作用的重要因素[12]。将以上四个因素依次输入RCO程序,通过随机选择得到九组随机试验条件(表1)。依据四个因素的因子值进行乳酸菌粘附数量测定,结果见表1。其中试验2与试验9得到的粘附数量值显著高于其他组(P<0.05),该因子组合条件有利于聚焦后续优化范围。由于粘附数量值的数量级相差太大导致优化目标值范围太大,无法精准聚焦,故将乳酸菌粘附数量值归一化后再输入RCO程序进行下一步质心搜索。
表 1 随机搜索试验设计Table 1. Design of random search experiment编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液
pH乳酸菌粘附数量
(105 CFU/g)1 3.22(103) 21.03(21) 10.60(11) 3.78(3.8) 0.08a 2 7.80(108) 22.45(22) 17.07(17) 7.76(7.8) 1100.00d 3 6.70(107) 13.42(13) 10.93(11) 5.81(5.8) 230.33b 4 3.68(104) 9.31(9) 29.35(29) 6.68(6.7) 0.43a 5 7.69(108) 7.79(8) 17.06(17) 6.72(6.7) 542.00c 6 7.37(107) 6.28(6) 28.10(28) 6.64(6.6) 124.67b 7 3.34(103) 13.02(13) 28.10(28) 7.12(7.1) 0.06a 8 3.96(104) 11.99(12) 16.02(16) 4.34(4.3) 0.32a 9 7.64(108) 19.87(20) 7.41(7) 4.91(4.9) 1253.33e 注:编号及其对应的不同因素值由随机质心映射程序设计;括号中的值是四舍五入处理后的值,即直接用于后续试验的条件值;字母a~e表示同一列中不同字母的平均值具有显著差异(P<0.05)。 2.2 质心搜索试验
RCO程序经过质心搜索试验设计,提出了四组新的因素水平值组合(表2)。按照质心搜索试验条件,再次测定凡纳滨对虾表面的乳酸菌粘附数量,结果见表2。试验结果具有显著差异,且试验组11中的乳酸菌粘附数量显著高于其他组(P<0.05),这可能与较高的接种液浓度增加了单位面积下乳酸菌Lac 9-3与凡纳滨对虾表面的接触有关。归一化后的粘附数量值被再此输入RCO程序进行映射优化。
表 2 质心搜索试验设计Table 2. Design of centroid search experiment编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液
pH乳酸菌粘附数量
(107 CFU/g)10 7.46(107) 15.88(16) 13.12(13) 6.30(6.3) 3.70b 11 7.63(108) 14.10(14) 17.41(17) 6.51(6.5) 31.87c 12 7.38(107) 15.51(16) 15.88(16) 6.28(6.3) 1.39a 13 7.35(107) 11.84(12) 15.88(16) 6.02(6.0) 3.70b 注:编号及其对应的不同因素值由随机质心映射程序设计;括号中的值是四舍五入处理后的值,即直接用于后续试验的条件值;字母a~c表示同一列中不同字母的平均值具有显著差异(P<0.05)。 2.3 映射优化试验
由于图1中趋势线清晰可见、箭头与趋势线指向明确,故针对本试验一轮RCO循环周期即可完成。最终的优化映射为乳酸菌Lac 9-3在凡纳滨对虾表面的粘附性提供了一组最优的接种条件,X轴箭头分别指向四个因素的最优水平值,即在接种液浓度为108 CFU/mL、菌株生长阶段为14.1 h(对应生长曲线中的稳定期初期),浸泡时间为17.41 min,接种液pH为6.51的条件下,可实现乳酸菌Lac 9-3在凡纳滨对虾表面的最高粘附性。并且在映射中,接种液浓度和菌株生长阶段呈现出更多的趋势线(图1中的直线和曲线均为趋势线),并明确地指向该因素的最佳值,表明乳酸菌Lac 9-3的粘附性受接种液浓度和菌株生长阶段的影响很大,而受浸泡时间和接种液pH的影响较小。类似地,谢琼[26]也发现接种液浓度与菌株生长阶段是影响植物乳杆菌ZDY 2013(L. plantarum)粘附性的关键因素。
已有研究表明随接种液浓度增大,乳酸菌的粘附数量增加,但当接种液浓度增加至一定值后,其粘附数量趋于稳定[27]。如当接种液浓度达到2×108 CFU/mL,乳酸菌的粘附数量不再发生显著变化,这可能与乳酸菌在宿主表面达到饱和占位状态有关[26]。大量研究显示,当乳酸菌生长至稳定期初期时,菌体生长稳定,且代谢产生较多的粘附素等大分子物质,有利于乳酸菌在宿主表面的粘附[12]。一般情况下,在偏酸性或中性条件下乳酸菌的粘附性更高,例如Yadav等[28]研究发现在pH6时植物乳杆菌91(L. plantarum)更易粘附于胶原蛋白表面。总之,以上结果表明接种液浓度、菌株生长阶段等自身性质与浸泡时间、接种液pH等外界条件都是影响乳酸菌粘附性的关键因素,且具有菌株特异性。因此,选择适宜的接种条件,特别是接种液浓度和菌株生长阶段,将为提升乳酸菌在生物防治、食品发酵等方面的作用效果指明方向。
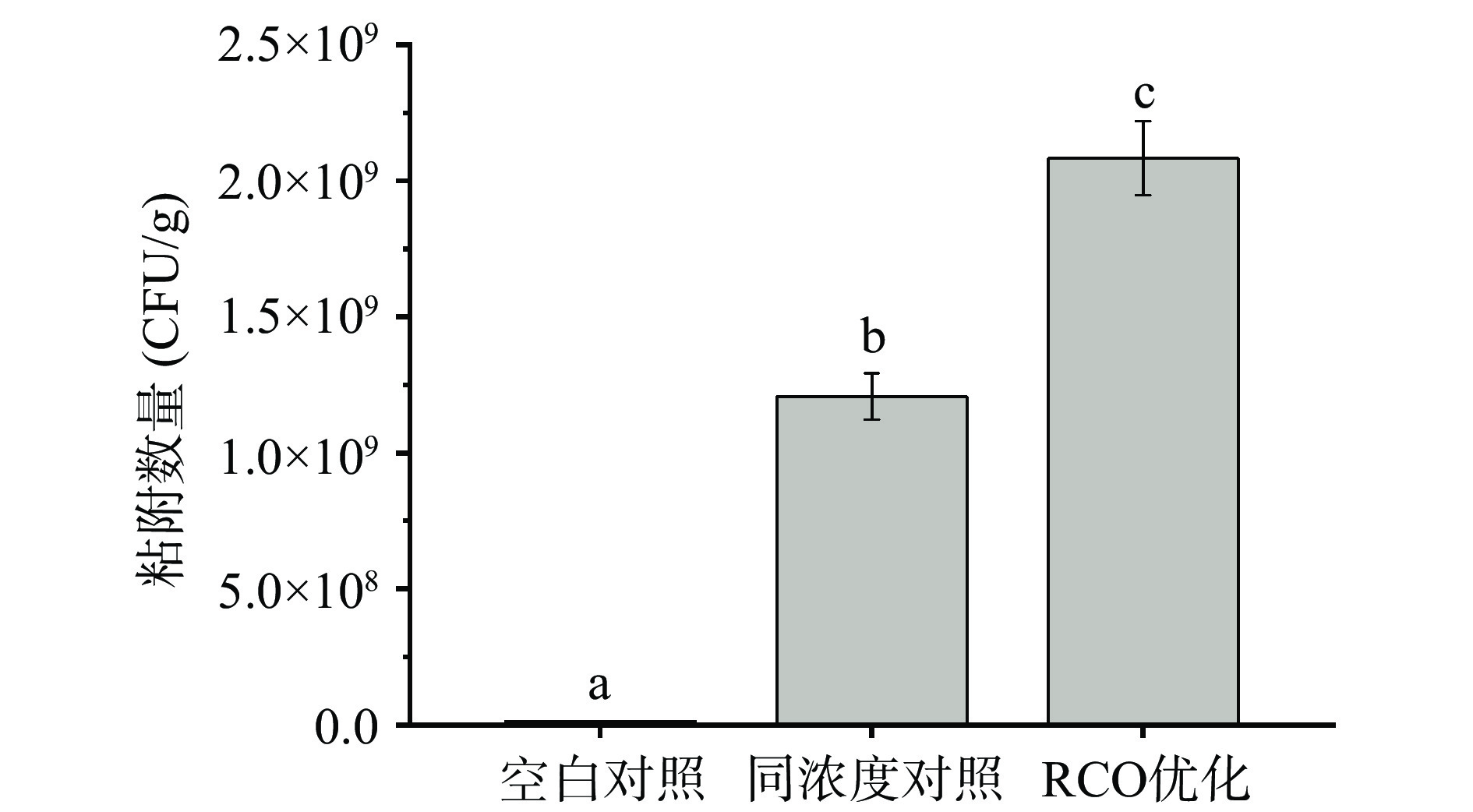
2.4 验证试验
为验证RCO优化对乳酸菌Lac 9-3在凡纳滨对虾表面粘附数量的提升效果(表3),设置空白对照组(试验组14)、同浓度对照组(试验组15)和RCO优化组(试验组16)再次进行乳酸菌粘附数量测定,结果如图2所示。显然,RCO优化后的粘附数量达到2.08×109 CFU/g,显著高于空白对照组和同浓度对照组(P<0.05),并且较同浓度对照组粘附数量增加72.65%。因此,RCO试验结果准确可靠。
表 3 RCO优化前后对比试验设计Table 3. Experimental design before and after RCO optimization comparison编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液pH 14 106 12 20 − 15 108 12 20 − 16 108 14 17 6.5 2.5 乳酸菌Lac 9-3对冷藏凡纳滨对虾菌群结构的影响
2.5.1 稀释曲线
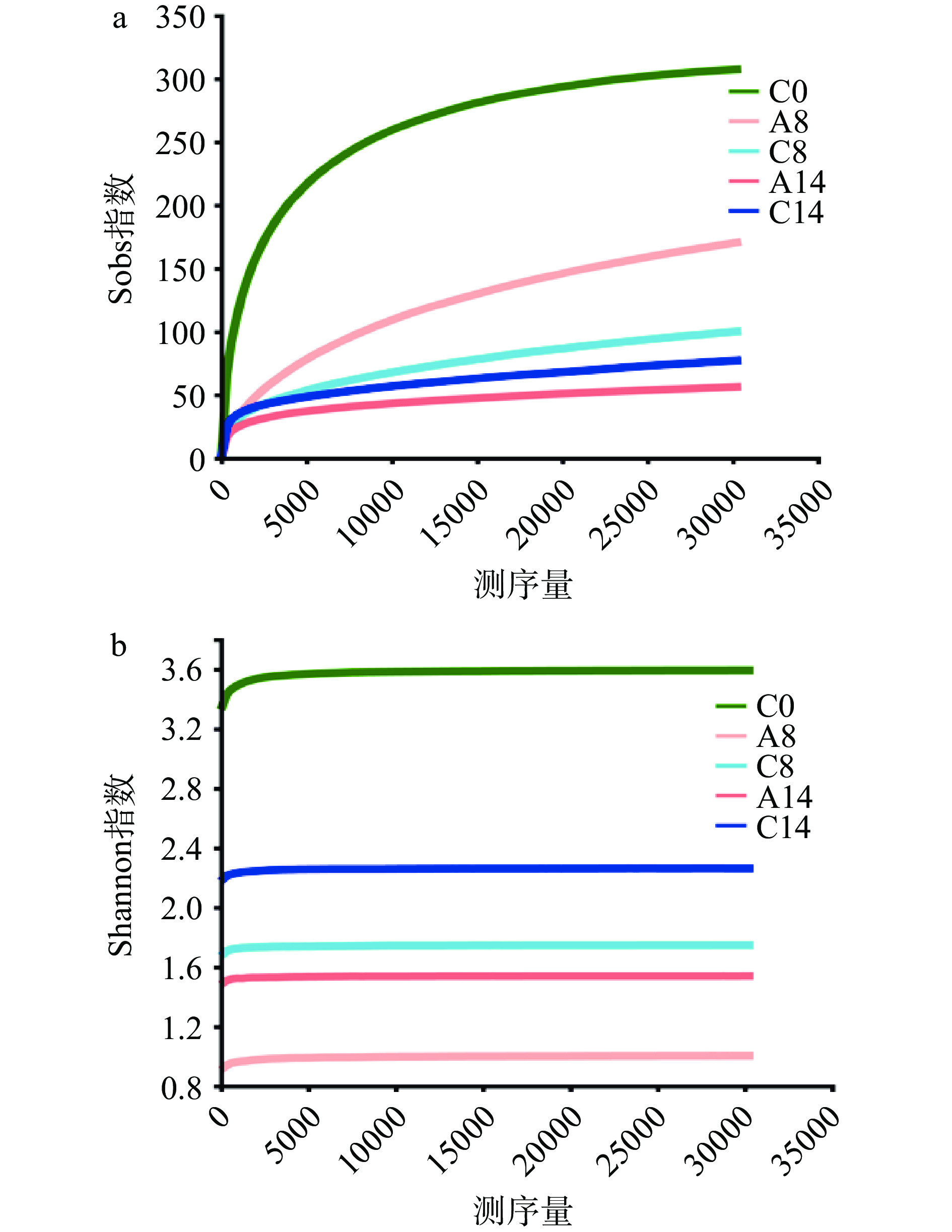
图3中Sobs曲线显示随测序量增加,曲线幅度趋于平缓,说明更多的测序数据只会对OTU聚类产生较小影响,因此目前的测序深度足以反映样品中微生物的物种丰富度。Shannon曲线是另一种评价测序深度的指标。当测序量足够大时,样品的物种多样性不再发生变化,说明现有的测序量可反映样品中物种信息,足够满足后续的生信分析。
2.5.2 物种多样性
Alpha多样性指数是评价微生物群落丰富度和多样性的关键指标[29]。本文以Coverage指数(覆盖度)、Sobs指数(实际观测到的OTU数目)、Chao指数与Ace指数(丰富度指数)为代表[30]来评价冷藏凡纳滨对虾菌群结构变化,结果见表4。本研究结果中Coverage指数值均大于0.99,表明测序深度足以反映各组样本中微生物区系的真实情况,与稀释曲线结果一致。Sobs、Chao和Ace指数均呈现相同的变化趋势:随贮藏时间延长,Alpha多样性指数降低,这可能归因于低温对部分嗜温性微生物的生长繁殖产生了抑制作用,进而影响凡纳滨对虾的微生物群落组成[31]。此外,腐败菌及其产生的有害代谢产物也会导致微生物丰富度和多样性下降。这与陶飞燕等[29]关于微冻凡纳滨对虾中微生物种类的研究结果基本一致,结果均显示随低温贮藏时间延长,凡纳滨对虾样品中的微生物种类趋于简化。如贮藏8 d时,乳酸菌Lac 9-3处理组的Alpha多样性指数(Sobs、Ace、Chao指数)均显著高于对照组,说明乳酸菌Lac 9-3处理可显著抑制冷藏过程中菌群丰富度的下降(P<0.05)。贮藏14 d时,对照组的Sobs、Ace、Chao指数值反而更高,这可能与乳酸菌Lac 9-3对冷藏过程中微生物群落演替的影响有关。
表 4 凡纳滨对虾样品的Alpha多样性指数结果Table 4. Alpha diversity index results for L. vannamei samples多样性
指数0 d
新鲜样品8 d 14 d Lac 9-3 对照 Lac 9-3 对照 Coverage 0.999 0.998 0.999 0.999 0.999 Sobs 307.5±0.5d 171.0±14.0c 100.5±9.5b 56.5±3.5a 77.5±4.5ab Ace 319.7±8.0c 236.9±12.7bc 147.0±7.4ab 86.4±0.4a 169.9±52.9ab Chao 315.4±5.8c 223.6±15.2b 138.0±14.0ab 114.7±43.3a 115.1±25.0a 注:字母a-d表示同一行中不同字母的平均值具有显著差异(P<0.05)。 2.5.3 物种组成
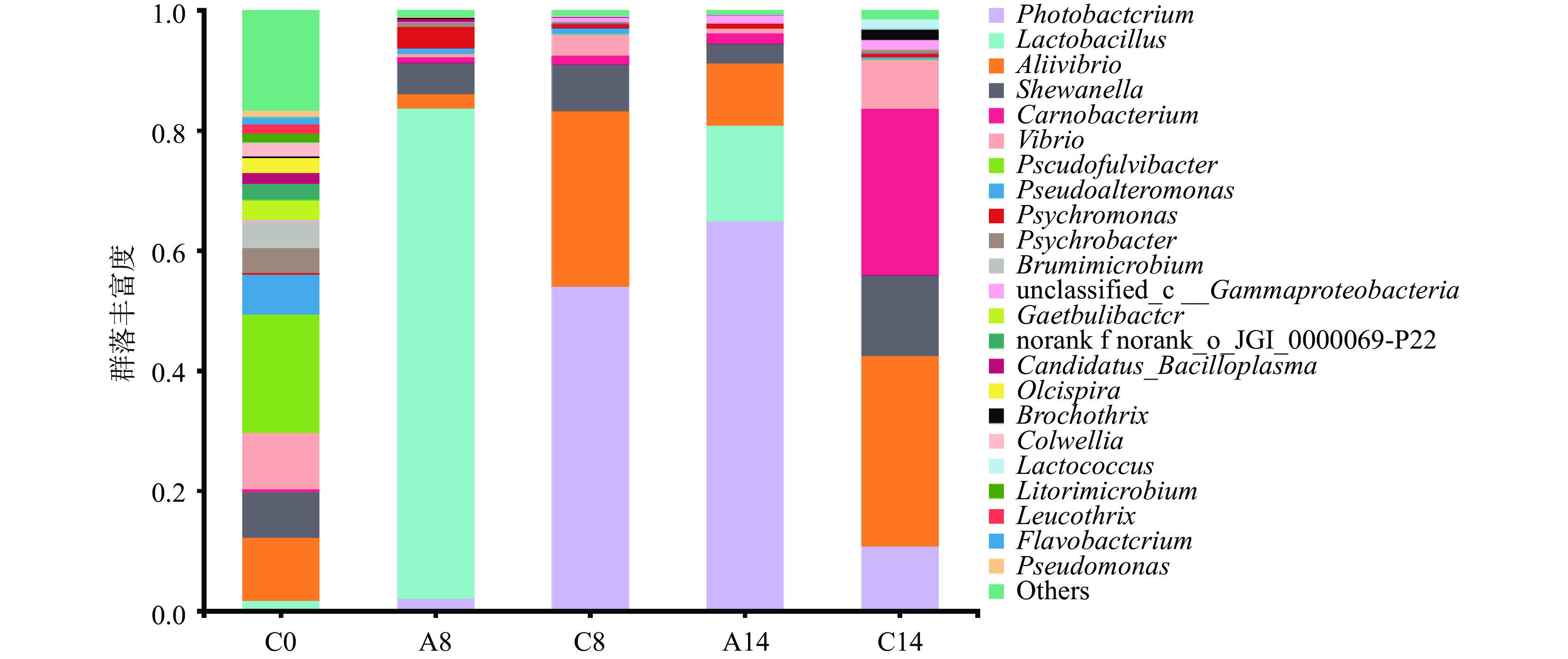
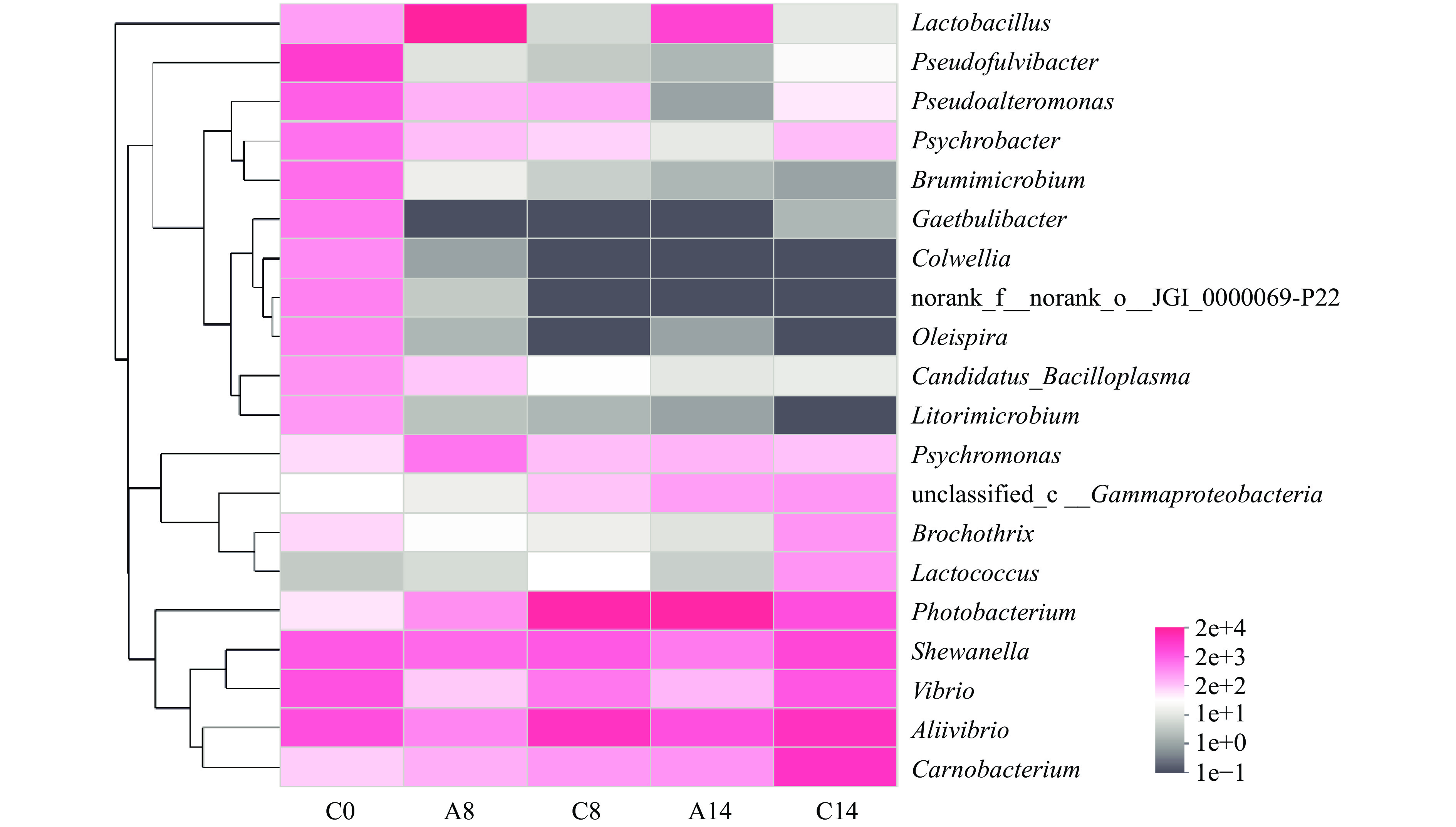
在属水平上(图4),新鲜凡纳滨对虾中的优势菌群为假黄杆菌属(Pseudofulvibacter)、别弧菌属(Aliivibrio)、弧菌属(Vibrio)和希瓦氏菌属(Shewanella),这与杨胜平等[32]的研究结果基本一致。本研究结果显示,冷藏8 d后,对照组样品中别弧菌属(Aliivibrio)、发光杆菌属(Photobacterium)和希瓦氏菌属(Shewanella)相对丰度显著增加,而乳酸菌Lac 9-3处理组样品中的别弧菌属(Aliivibrio)、发光杆菌属(Photobacterium)和希瓦氏菌属(Shewanella)相对丰度均显著低于对照组,原因可能是乳酸菌Lac 9-3在凡纳滨对虾表面占据粘附位点并大量繁殖,抑制了腐败菌的迅速生长。冷藏14 d后,对照组中优势菌属依次为别弧菌属(Aliivibrio)、肉食杆菌属(Carnobacterium)、希瓦氏菌属(Shewanella),比例分别为31.7%、27.7%和13.5%,说明这些菌在4 ℃条件下能继续繁殖,是冷藏凡纳滨对虾中的优势腐败菌。与对照组相比,乳酸菌Lac 9-3处理组样品中别弧菌属(Aliivibrio)、肉食杆菌属(Carnobacterium)、希瓦氏菌属(Shewanella)在冷藏后期占菌群中的比例分别低至10.4%、1.8%和3.2%,说明乳酸菌Lac 9-3有效抑制了优势腐败菌的生长,减少了胺类有害物质的积累,推测其可通过改变腐败菌菌群结构延缓凡纳滨对虾的腐败进程。
![]() 图 4 凡纳滨对虾样品微生物物种组成(属水平)注:C0表示新鲜对虾样本,A8表示乳酸菌Lac 9-3处理组冷藏8 d样本,C8表示对照组冷藏8 d样本,A14表示乳酸菌Lac 9-3处理组冷藏14 d样本,C14表示对照组冷藏14 d样本;图5同。Figure 4. Microbial species composition of Litopenaeus vannamei samples at the genus level
图 4 凡纳滨对虾样品微生物物种组成(属水平)注:C0表示新鲜对虾样本,A8表示乳酸菌Lac 9-3处理组冷藏8 d样本,C8表示对照组冷藏8 d样本,A14表示乳酸菌Lac 9-3处理组冷藏14 d样本,C14表示对照组冷藏14 d样本;图5同。Figure 4. Microbial species composition of Litopenaeus vannamei samples at the genus level以属水平上的物种注释结果为依据,选取物种丰度排名前二十的属进行聚类,并绘制成热图。如图5所示,假黄杆菌属(Pseudofulvibacter)、布鲁士菌属(Brumimicrobium)、念珠菌属(Candidatus_Bacilloplasma)等大多数微生物随冷藏时间延长相对丰度降低,这与Alpha多样性指数的结果一致。在进化关系上,冷藏凡纳滨对虾的优势腐败菌(希瓦氏菌属(Shewanella)、肉食杆菌属(Carnobacterium)、别弧菌属(Aliivibrio)与弧菌属(Vibrio))不仅致腐能力强[31],进化关系也接近。因此,推测乳酸菌Lac 9-3可通过调控冷藏凡纳滨对虾的菌群结构,延缓优势腐败菌诱导的腐败变质过程,从而延长货架期。
3. 结论
本文采用随机质心映射优化法提升了乳酸菌Lac 9-3在凡纳滨对虾表面的粘附性,优化过程简单,试验次数少。确定乳酸菌Lac 9-3的最佳接种条件为:接种液浓度108 CFU/mL,菌株生长阶段14.1 h(对应稳定期初期),浸泡时间17.41 min,接种液pH6.51。经验证,乳酸菌粘附数量较同浓度对照组增加72.65%,优化效果显著。映射优化结果表明接种液浓度与菌株生长阶段是影响乳酸菌Lac 9-3粘附性的主要因素,这为乳酸菌在生物防治、食品发酵等方面的应用提供了参考。菌相结果显示乳酸菌Lac 9-3可抑制冷藏凡纳滨对虾表面优势腐败菌希瓦氏菌属(Shewanella)、肉食杆菌属(Carnobacterium)、别弧菌属(Aliivibrio)与弧菌属(Vibrio)的生长繁殖,调节凡纳滨对虾冷藏过程中的微生物群落组成。综上,生防乳酸菌Lac 9-3可通过改变冷藏凡纳滨对虾的菌群结构而影响其腐败变质进程,其在水产品保鲜领域具有广阔的应用前景。
-
图 4 凡纳滨对虾样品微生物物种组成(属水平)
注:C0表示新鲜对虾样本,A8表示乳酸菌Lac 9-3处理组冷藏8 d样本,C8表示对照组冷藏8 d样本,A14表示乳酸菌Lac 9-3处理组冷藏14 d样本,C14表示对照组冷藏14 d样本;图5同。
Figure 4. Microbial species composition of Litopenaeus vannamei samples at the genus level
表 1 随机搜索试验设计
Table 1 Design of random search experiment
编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液
pH乳酸菌粘附数量
(105 CFU/g)1 3.22(103) 21.03(21) 10.60(11) 3.78(3.8) 0.08a 2 7.80(108) 22.45(22) 17.07(17) 7.76(7.8) 1100.00d 3 6.70(107) 13.42(13) 10.93(11) 5.81(5.8) 230.33b 4 3.68(104) 9.31(9) 29.35(29) 6.68(6.7) 0.43a 5 7.69(108) 7.79(8) 17.06(17) 6.72(6.7) 542.00c 6 7.37(107) 6.28(6) 28.10(28) 6.64(6.6) 124.67b 7 3.34(103) 13.02(13) 28.10(28) 7.12(7.1) 0.06a 8 3.96(104) 11.99(12) 16.02(16) 4.34(4.3) 0.32a 9 7.64(108) 19.87(20) 7.41(7) 4.91(4.9) 1253.33e 注:编号及其对应的不同因素值由随机质心映射程序设计;括号中的值是四舍五入处理后的值,即直接用于后续试验的条件值;字母a~e表示同一列中不同字母的平均值具有显著差异(P<0.05)。 表 2 质心搜索试验设计
Table 2 Design of centroid search experiment
编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液
pH乳酸菌粘附数量
(107 CFU/g)10 7.46(107) 15.88(16) 13.12(13) 6.30(6.3) 3.70b 11 7.63(108) 14.10(14) 17.41(17) 6.51(6.5) 31.87c 12 7.38(107) 15.51(16) 15.88(16) 6.28(6.3) 1.39a 13 7.35(107) 11.84(12) 15.88(16) 6.02(6.0) 3.70b 注:编号及其对应的不同因素值由随机质心映射程序设计;括号中的值是四舍五入处理后的值,即直接用于后续试验的条件值;字母a~c表示同一列中不同字母的平均值具有显著差异(P<0.05)。 表 3 RCO优化前后对比试验设计
Table 3 Experimental design before and after RCO optimization comparison
编号 接种液浓度
(CFU/mL)菌株生长阶段
(h)浸泡时间
(min)接种液pH 14 106 12 20 − 15 108 12 20 − 16 108 14 17 6.5 表 4 凡纳滨对虾样品的Alpha多样性指数结果
Table 4 Alpha diversity index results for L. vannamei samples
多样性
指数0 d
新鲜样品8 d 14 d Lac 9-3 对照 Lac 9-3 对照 Coverage 0.999 0.998 0.999 0.999 0.999 Sobs 307.5±0.5d 171.0±14.0c 100.5±9.5b 56.5±3.5a 77.5±4.5ab Ace 319.7±8.0c 236.9±12.7bc 147.0±7.4ab 86.4±0.4a 169.9±52.9ab Chao 315.4±5.8c 223.6±15.2b 138.0±14.0ab 114.7±43.3a 115.1±25.0a 注:字母a-d表示同一行中不同字母的平均值具有显著差异(P<0.05)。 -
[1] LI Y, LEI Y T, TAN Y Q, et al. Efficacy of freeze-chilled storage combined with tea polyphenol for controlling melanosis, quality deterioration, and spoilage bacterial growth of Pacific white shrimp (Litopenaeus vannamei)[J]. Food Chemistry,2022,370:130924. doi: 10.1016/j.foodchem.2021.130924
[2] DO D T B, BUI T H, PHAN D T A. Persea americana Mill seed extracts: Understanding insights into the antioxidant and antityrosinase activities and effects on preserving qualities of whiteleg shrimp (Litopenaus vannamei) during refrigerated storage[J]. Food Chemistry,2021,373:131469.
[3] QIU L Q, ZHANG M, BHANDARI B, et al. Shelf life extension of aquatic products by applying nanotechnology[J]. Critical Reviews in Food Science and Nutrition,2022,62(6):1521−1535. doi: 10.1080/10408398.2020.1844139
[4] BARCENILLA C, DUCIC M, LÓPEZ M, et al. Application of lactic acid bacteria for the biopreservation of meat products: A systematic review[J]. Meat Science,2022,183:108661. doi: 10.1016/j.meatsci.2021.108661
[5] RATHOD N B, PHADKE G G, TABANELLI G, et al. Recent advances in bio-preservatives impacts of lactic acid bacteria and their metabolites on aquatic food products[J]. Food Bioscience,2021,44:101440. doi: 10.1016/j.fbio.2021.101440
[6] 杨伟杰, 鞠慧丽. 乳酸菌在水产品保鲜的应用[J]. 食品界,2018(8):81. [YANG W J, JU H L. Application of lactic acid bacteria in the preservation of aquatic products[J]. Food Industry,2018(8):81. YANG W J, JU H L. Application of lactic acid bacteria in the preservation of aquatic products[J]. Food Industry, 2018(8): 81.
[7] 丁诗瑶, 雷文平, 刘成国, 等. 乳酸菌细胞表面结构与胃肠道的相互作用[J]. 食品与机械,2020,36(4):40−44. [DING S Y, LEI W P, LIU C G, et al. Cell surface structure of lactic acid bacteria and its interaction with gastrointestinal tract[J]. Food & Machinery,2020,36(4):40−44. DING S Y, LEI W P, LIU C G, et al. Cell surface structure of lactic acid bacteria and its interaction with gastrointestinal tract[J]. Food & Machinery, 2020, 36(4): 40-44.
[8] GUAN C R, CHEN X, JIANG X R, et al. In vitro studies of adhesion properties of six lactic acid bacteria isolated from the longevous population of China[J]. Royal Society of Chemistry Advances,2020,10:24234−24240.
[9] HOJJATI M, BEHABAHANI B A, FALAH F. Aggregation, adherence, anti-adhesion and antagonistic activity properties relating to surface charge of probiotic Lactobacillus brevis gp104 against Staphylococcus aureus[J]. Microbial Pathogenesis,2020,147:104420. doi: 10.1016/j.micpath.2020.104420
[10] SAID L B, GAUDREAU H, DALLAIRE L, et al. Bioprotective culture: A new generation of food additives for the preservation of food quality and safety[J]. Industrial Biotechnology,2019,15(3):138−147. doi: 10.1089/ind.2019.29175.lbs
[11] FATEN K, HAMIDA K, SOUMYA E A, et al. Lactobacillus plantarum: Effect of a protective biofilm on the surface of olives during storage[J]. Brazilian Journal of Microbiology,2016,47(1):202−209. doi: 10.1016/j.bjm.2015.11.028
[12] 占萌, 李春, 李慧臻, 等. 乳酸菌粘附肠道上皮细胞的研究进展[J]. 中国食品学报,2020,20(11):10. [ZHAN M, LI C, LI H Z, et al. The research progress on the adherence of lactic acid bacteria to intestinal epithelial cells[J]. Journal of Chinese Institute of Food Science and Technology,2020,20(11):10. ZHAN M, LI C, LI H Z, et al. The research progress on the adherence of lactic acid bacteria to intestinal epithelial cells[J]. Journal of Chinese Institute of Food Science and Technology, 2020, 20(11): 10.
[13] BAO J, ZHANG X, ZHENG J H, et al. Mixed fermentation of Spirulina platensis with Lactobacillus plantarum and Bacillus subtilis by random-centroid optimization[J]. Food Chemistry,2018,264(OCT.30):64−72.
[14] XIN L Y, GUO L M, EDIRS S, et al. An efficient deacidification process for safflower seed oil with high nutritional property through optimized ultrasonic-assisted technology[J]. Molecules,2022,27:2305. doi: 10.3390/molecules27072305
[15] 郑小善, 吉宏武, 张泽伟, 等. 热风干制前后凡纳滨对虾中脂质及其脂肪酸组成变化[J]. 食品工业科技,2022,43(10):87−93. [ZHEN X S, JI H W, ZHANG Z W, et al. Changes of lipid and fatty acid composition in shrimps (Litopenaeus vannamei) before and after hot-air-drying[J]. Science and Technology of Food Industry,2022,43(10):87−93. ZHEN X S, JI H W, ZHANG Z W, et al. Changes of lipid and fatty acid composition in shrimps (Litopenaeus vannamei) before and after hot-air-drying[J]. Science and Technology of Food Industry, 2022, 43(10): 87-93.
[16] LI J P, YANG X Y, SHI G C, et al. Cooperation of lactic acid bacteria regulated by the AI-2/LuxS system involve in the biopreservation of refrigerated shrimp[J]. Food Research International,2019,120:679−687. doi: 10.1016/j.foodres.2018.11.025
[17] NAKAI S, DOU J L, LO K V, et al. Optimization of site-directed mutagenesis. 1. New random-centroid optimization program for windows useful in research and development[J]. Journal of Agricultural & Food Chemistry,1998,46(4):1642−1654.
[18] 任大勇. 益生乳酸杆菌的黏附及免疫调节作用研究[D]. 长春: 吉林大学, 2013. REN D Y. Research on adhesion and immunoregulation of probiotic Lactobacillus strains[D]. Changchun: Jilin University, 2013.
[19] 王嘉悦. 枸杞多糖与益生菌粘附特性关系的研究[D]. 北京: 北京林业大学, 2019. WANG J Y. Study of adhesion characteristics of Lycium barbarum polysaccharides and probiotics[D]. Beijing: Beijing Forestry University, 2019.
[20] 李冉, 朱和源, 叶可萍, 等. 气调包装狮子头冷藏过程中微生物变化及菌群结构分析[J]. 食品工业科技,2021,42(11):99−105. [LI R, ZHU H Y, YE K P, et al. Analysis of microbial counts and bacterial community in modified atmosphere packaging meatballs[J]. Science and Technology of Food Industry,2021,42(11):99−105. LI R, ZHU H Y, YE K P, et al. Analysis of microbial counts and bacterial community in modified atmosphere packaging meatballs[J]. Science and Technology of Food Industry, 2021, 42(11): 99-105.
[21] CHEN S F, ZHOU Y Q, CHEN Y R, et al. Fastp: An ultra-fast all-in-one FASTQ preprocessor[J]. Cold Spring Harbor Laboratory,2018,34(17):i884−i890.
[22] 唐林, 郭柯宇, 赖鲸慧, 等. 屠宰过程中猪胴体表面及环境的细菌菌相分析[J]. 食品科学,2022,43(12):203−209. [TANG L, GUO K Y, LAI J H, et al. Investigation of bacterial flora on the surface of pig carcasses and in the environment during slaughter[J]. Food Science,2022,43(12):203−209. TANG L, GUO K Y, LAI J H, et al. Investigation of bacterial flora on the surface of pig carcasses and in the environment during slaughter[J]. Food Science, 2022, 43(12): 203-209.
[23] YANG J, YANG X Y, LIANG R R. The response of bacterial communities to carbon dioxide in high-oxygen modified atmosphere packaged beef steaks during chilled storage[J]. Food Research International,2022,151:110872. doi: 10.1016/j.foodres.2021.110872
[24] WU G P, LI Z H, ZHENG Y. Supplementing cholamine to diet lowers laying rate by promoting liver fat deposition and altering intestinal microflora in laying hens[J]. Poultry Science,2022,101(10):102084. doi: 10.1016/j.psj.2022.102084
[25] LI J, WEI Q, HUANG L X, et al. Mathematical modeling Pseudomonas spp. growth and microflora composition variation in Agaricus bisporus fruiting bodies during chilled storage[J]. Postharvest Biology and Technology,2020,163:111144. doi: 10.1016/j.postharvbio.2020.111144
[26] 谢琼. 植物乳杆菌ZDY2013表层蛋白及其益生特性的初步探究[D]. 南昌: 南昌大学, 2017. XIE Q. Research on the surface layer protein and probiotic functions of Lactobacillus plantarum ZDY2013[D]. Nanchang: Nanchang University, 2017.
[27] 佘银, 罗芳, 高婉茹, 等. 乳酸菌粘附特性的研究新进展[J]. 食品研究与开发,2018,39(4):7. [SHE Y, LUO F, GAO W R, et al. The new advance of research on the adhesion of Lactobacillus[J]. Food Research and Development,2018,39(4):7. doi: 10.3969/j.issn.1005-6521.2018.04.002 SHE Y, LUO F, GAO W R, et al. The new advance of research on the adhesion of Lactobacillus[J]. Food Research and Development, 2018, 39(4): 7. doi: 10.3969/j.issn.1005-6521.2018.04.002
[28] YADAV A K, TYAGI A, KAUSHIK J K, et al. Role of surface layer collagen binding protein from indigenous Lactobacillus plantarum 91 in adhesion and its anti-adhesion potential against gut pathogen[J]. Microbiological Research,2013,168(10):39−645.
[29] 陶飞燕, 潘创, 陈胜军, 等. 基于高通量测序技术分析微冻凡纳滨对虾的微生物[J]. 南方水产科学,2021,17(2):10. [TAO F Y, PAN C, CHEN S J, et al. Microbial analysis of Litopenaeus vannamei during partial freezing storage by Illumina high throughput sequencing[J]. South China Fisheries Science,2021,17(2):10. TAO F Y, PAN C, CHEN S J, et al. Microbial analysis of Litopenaeus vannamei during partial freezing storage by Illumina high throughput sequencing[J]. South China Fisheries Science, 2021, 17(2): 10.
[30] YAO Y P, ZHOU X Y, HADIATULLAH H, et al. Determination of microbial diversities and aroma characteristics of Beitang Litopenaeus vannamei paste[J]. Food Chemistry,2020,344:128695.
[31] 周涛, 吴晓营, 罗海波, 等. 贮藏温度对即食小龙虾品质及微生物菌群多样性的影响[J]. 食品与机械,2019(9):6. [ZHOU T, WU X Y, LUO H B, et al. Analysis of quality and colony diversity of products of crayfish under different storage temperatures[J]. Food & Machinery,2019(9):6. ZHOU T, WU X Y, LUO H B, et al. Analysis of quality and colony diversity of products of crayfish under different storage temperatures[J]. Food & Machinery, 2019(9): 6.
[32] 杨胜平, 谢晶, 钱韻芳. 基于16S rRNA的高通量测序和DGGE法对比新鲜与4 ℃贮藏腐败的凡纳滨对虾微生物菌群变化[J]. 中国食品学报,2018,18(9):280−287. [YANG S P, XIE J, QIAN Y F. Comparative analysis of microbial communities of fresh and spoiled Pacific White shrimp stored at 4 ℃ by 16S rRNA-based pyrosequencing and DGGE[J]. Journal of Chinese Institute of Food Science and Technology,2018,18(9):280−287. YANG S P, XIE J, QIAN Y F. Comparative analysis of microbial communities of fresh and spoiled Pacific White shrimp stored at 4 ℃ by 16S rRNA-based pyrosequencing and DGGE[J]. Journal of Chinese Institute of Food Science and Technology, 2018, 18(9): 280-287.
-
期刊类型引用(3)
1. 张敏杰,杨武德,代叶,李玮,魏晴,梁珊珊. 黔产不同商品规格金钗石斛质量评价研究. 亚太传统医药. 2024(04): 39-43 .  百度学术
百度学术
2. 林鑫静,张明,李鑫,周春阳,蒲跃,袁斌,范艺缤,范润勇,夏天琴,尤俊,杨晓曦,胥正敏. 调脏舒秘合剂小鼠急性毒性实验研究. 现代中医药. 2023(02): 91-95 .  百度学术
百度学术
3. 杨吉容,石京山. 金钗石斛破壁粉对自发性高血压大鼠血压及心功能的影响. 遵义医科大学学报. 2022(06): 699-705 .  百度学术
百度学术
其他类型引用(2)





 下载:
下载:
 下载:
下载:
