Mechanism of Baicalein Inhibiting the PD-1/PD-L1 Interaction Based on Molecular Dynamics Simulation and Experiment Research
-
摘要: 为研究黄芩素阻断程序性细胞死亡-1/程序性细胞死亡配体1(PD-1/PD-L1)通路的分子机制,本文首先采用分子对接、分子动力学模拟、结合自由能计算和主成分分析等方法预测了黄芩素的抑制作用,然后利用酶联免疫吸附试验(ELISA)进行了实验验证。结合自由能结果表明,黄芩素与PD-L1二聚体(PD-L1 dimer)的结合亲和力为−32.41±0.31 kcal/mol。结合能分解、接触数和非键相互作用结果显示,黄芩素主要结合在PD-L1 dimer的C-、C'-、F-和G-sheet区域,其中关键残基Tyr56、Met115、Ala121和Asp122与黄芩素之间的非极性相互作用在结合过程中起主导作用。互相关矩阵和二级结构结果进一步表明,黄芩素可与PD-L1 dimer的sheet区域稳定结合。ELISA结果显示黄芩素对PD-1/PD-L1相互作用抑制率的IC50为79.47 µg/L。黄芩素可通过直接与PD-L1 dimer结合抑制PD-1/PD-L1相互作用,本研究为该通路天然小分子抑制剂的发现提供了依据。
-
关键词:
- 程序性细胞死亡-1/程序性细胞死亡配体1 /
- 天然小分子 /
- 黄芩素 /
- 分子动力学模拟 /
- 抑制机制
Abstract: To study the molecular mechanism of baicalein interrupting the programmed cell death-1 (PD-1) and programmed cell death-ligand 1 (PD-L1) pathway, molecular docking, molecular dynamics simulation, binding free energy calculation and principal component analysis were first performed to predict the inhibition effect of baicalein on this pathway, which was verified by enzyme-linked immunosorbent assay (ELISA) subsequently. Binding free energy calculations showed that the affinity of baicalein to the PD-L1 dimer was −32.41±0.31 kcal/mol. Free energy decomposition, contact numbers and nonbonded interaction results revealed that baicalein mainly interacted with the C-, C'-, F- and G-sheet domains of the PD-L1 dimer. Importantly, nonpolar interactions between the key residues Tyr56, Met115, Ala121, Asp122 and baicalein were dominant factors during the binding process. Cross-correlation matrixes and secondary structure results further demonstrated that baicalein could stably interact with the sheet domains of the PD-L1 dimer. The result of ELISA showed that the IC50 value of baicalein for inhibiting the PD-1/PD-L1 interaction was 79.47 µg/L. In conclusion, this study revealed that baicalein could directly bind to the PD-L1 dimer, thus blocking the PD-1/PD-L1 interaction, would provide basis for discovering natural small-molecule inhibitors of this pathway. -
程序性细胞死亡-1(programmed cell death-1,PD-1)是一种重要的免疫检查点蛋白,可通过与配体PD-L1(programmed cell death ligand 1)结合抑制T细胞增殖,从而起到负向免疫调控作用以维持机体的免疫稳态[1]。然而肿瘤细胞能够通过过量表达PD-L1逃避机体的免疫监视,从而快速增殖、转移。因此阻断PD-1/PD-L1通路可逆转机体的免疫抑制状态,有助于提高T细胞对肿瘤细胞的杀伤力[2]。实际上,目前已有大量靶向PD-1或PD-L1的单抗抑制剂上市,且这些抑制剂在多种肿瘤临床治疗中取得了突破性进展[3],但单抗由于其较大的分子量而存在肿瘤渗透性差、稳定性低以及研发成本高等局限性[4−6]。小分子(MW<550 Da)抑制剂因可克服上述缺点而受到广泛关注。2015年,百时美施贵宝公司报道了一系列抑制活性较好(IC50为0.92 nmol/L~14.25 µmol/L)合成小分子。之后,Zak团队阐明了该类小分子的抑制机制,指出小分子可作用于PD-L1表面并诱导PD-L1的二聚最终结合到二聚体的内表面,从而阻断该通路[7−8]。
相比之下,天然的小分子抑制剂具有生物活性多样、毒副作用低和来源广泛等特点,为该通路抑制剂的发现提供了巨大宝库[9]。黄芩素是一种天然黄酮类化合物,已有研究报道其可通过调控PD-L1表达抑制PD-1/PD-L1水平[10−11],然而关于其能否直接抑制PD-1/PD-L1相互作用及分子机制的研究鲜有报道。分子动力学模拟是利用计算机软件,以经典力学为基础、分子随时间变化的动态行为为模拟对象的一种方法,是研究分子间相互作用的重要工具[12]。事实上,分子动力学模拟已成功应用于PD-1/PD-L1通路的研究。如Sun等[13]和Shi等[14]利用分子动力学模拟的方法研究了PD-L1与单抗的作用机制,发现PD-L1的CC'FG结构域为主要结合区域。Verdura等[15]通过分子动力学模拟发现白藜芦醇可直接结合到PD-L1 dimer内表面从而阻断PD-1/PD-L1相互作用。此外,本课题组前期的分子动力学模拟研究表明姜黄素等天然小分子能够直接与PD-L1 dimer的关键残基结合从而抑制该通路[16−18]。
本文首先利用分子对接构建PD-L1 dimer/黄芩素复合物体系,然后借助GROMACS 2016.4软件进行150 ns的分子动力学模拟。通过分析结合自由能、接触数和非键相互作用等获得黄芩素与PD-L1 dimer的结合亲和力、作用位点及作用类型等信息,从理论层面掌握其直接抑制PD-1/PD-L1相互作用的分子机制。最后利用酶联免疫吸附试验(Enzyme-Linked Immunosorbent Assay,ELISA)对黄芩素的抑制作用进行验证,这些数据有助于指导该通路天然小分子抑制剂的发现。
1. 材料与方法
1.1 材料与仪器
黄芩素(纯度≥98%,HPLC) 上海源叶生物科技有限公司;PD-1酶联免疫分析试剂盒、人源PD-1标准品 本生(天津)健康科技有限公司。
SHJ-4A数显恒温磁力搅拌水浴锅 常州国语仪器制造有限公司;Multiskan FC型酶标仪 赛默飞世尔(上海)仪器有限公司。
1.2 实验方法
1.2.1 体系构建及分子对接
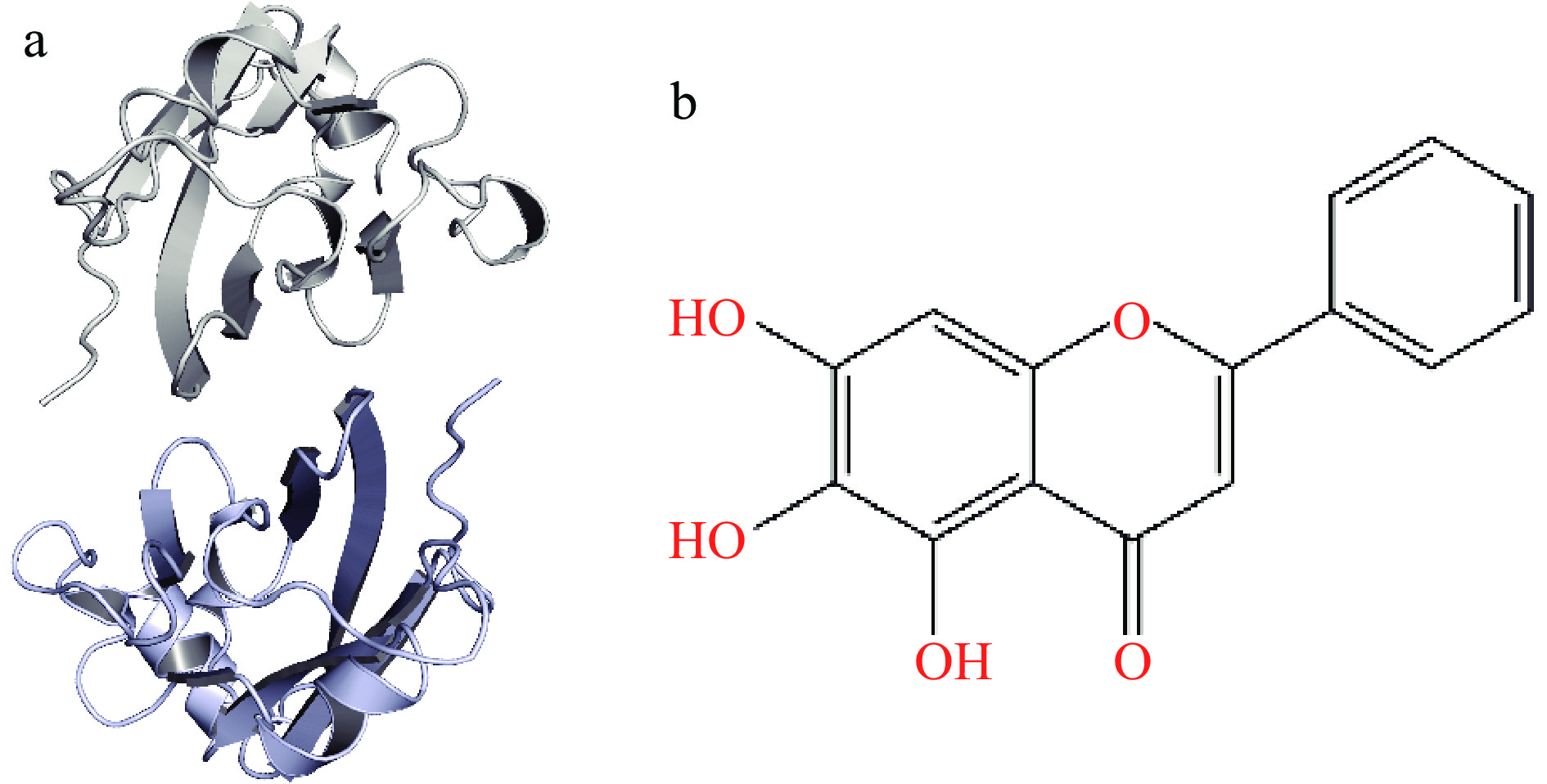
根据文献[7−8,15−16,18]调研结果,发现小分子抑制剂直接抑制PD-1/PD-L1相互作用的关键在于PD-L1 dimer的形成与稳定。基于此,首先从PDB数据库下载PD-L1 dimer/BMS-200(PDB ID:5N2F)和黄芩素(PDB ID:4X2A)的结构。删除水分子和配体BMS-200得到PD-L1 dimer,并运用WHAT IF服务器修复其缺失部分,黄芩素则在Chem3D软件的MM2力场下进行能量最小化,结构见图1。
然后利用AutoDock Tools分别对PD-L1 dimer和黄芩素进行加氢处理并生成pdbqt文件,使用Grid Box模块将盒子大小设为20 Å×20 Å×20 Å,格点间距设为1 Å,其他参数均设为默认值,最后运行AutoDock Vina软件进行分子对接[19]。选择结合亲和力最强的对接构象作为分子动力学模拟的初始结构。运用PyMOL软件可视化对接结果,构建相互作用3D模式图。为了考察黄芩素对PD-L1 dimer构象的影响,分别构建含黄芩素和不含黄芩素的体系。为了简便,将两个体系分别称为复合物和Dimer,PD-L1 dimer的两条链则分别命名为APD-L1和BPD-L1。
1.2.2 分子动力学模拟
使用GROMACS 2016.4软件进行分子动力学模拟,分别采用Amber ff99SB[20]和GAFF[21]描述蛋白和小分子的力场参数。首先将黄芩素和Dimer体系置于立方体的溶剂盒子,并保证体系原子到盒子边缘的距离不小于10 Å,随后添加抗衡离子以保证体系呈电中性。紧接着采用最陡下降法和共轭梯度法对各体系进行能量最小化,以使体系达到收敛状态。然后依次进行1 ns的NVT和1 ns的NPT平衡,使用V-rescale耦合方法将温度维持在300 K,使用Parrinello-Rahma方法将压力维持在1 atm。最后,体系在相同的参数下进行150 ns的模拟,并将快照以1.0 ps为时间间隔保存至轨迹用于后续分析。模拟过程中,短程非键相互作用的截断距离设为10 Å,长程静电相互作用的计算采用Particle Mesh Ewald(PME)算法,氢原子的约束使用LINCS算法。
1.2.3 结合自由能
采用分子力学泊松玻尔兹曼表面积法(molecular mechanics Poisson-Boltzmann surface area,MM-PBSA)计算各体系的结合自由能[22]。从动力学最后30 ns的平衡轨迹中采集300帧构象用于结合自由能(ΔG)计算,公式如下:
ΔG=Gcomplex−(Gprotein+Gligand) (1) G=EMM+Gsol−TΔS (2) EMM=Evdw+Eele (3) Gsol=EPB+ESA (4) ESA=γ⋅SASA (5) ΔG=ΔEvdw+ΔEele+ΔEPB+ΔESA (6) 式中,Gcomplex、Gprotein和Gligand分别代表蛋白-配体复合物、蛋白和配体的自由能;EMM代表气相中的分子力学能,包括范德华相互作用能(Evdw)和静电相互作用能(Eele);Gsol代表溶解自由能,可分解为极性溶解自由能(EPB)和非极性溶解自由能(ESA)两部分。前者通过求解泊松-玻尔兹曼(Poisson–Boltzmann,PB)方程获得,后者则通过计算分子表面面积(surface area,SA)而得,TΔS为熵变对结合自由能的贡献。由于本文关注结合自由能的相对值,且熵变的计算耗时较长,因此不考虑熵变的影响。为了解黄芩素与PD-L1 dimer作用过程中的关键残基,本文采用与前期研究相同的方法对结合自由能进行了分解[22−23]。
1.2.4 轨迹分析
使用GROMACS 2016.4内置分析工具和分子可视化程序1.9.3(Visual Molecular Dynamics,VMD)对模拟轨迹进行分析。使用mindist工具计算复合物体系的接触数,截断值设为6.0 Å。蛋白在模拟过程中二级结构的变化利用dictionary of secondary structure of proteins(DSSP 2.0.4)工具进行分析。采用主成分分析(principal component analysis,PCA)方法描述蛋白原子运动的相关性[24]。利用VMD程序计算复合物体系分子间氢键占有率[25],其中氢键的判定标准为受体-氢-供体的角度>135°且受体-氢原子的距离<3.5 Å。
1.2.5 ELISA
通过使用PD-1 ELISA试剂盒测定反应体系中PD-1含量,计算黄芩素对PD-1/PD-L1相互作用的抑制率。具体操作步骤包括加样:向空白孔、标准孔和待测样品孔分别加入二甲基亚砜、标准品和待测样品50 μL,37 ℃反应30 min;加酶:用洗涤液洗板5次,除空白孔外每孔加入酶标试剂50 μL,37 ℃反应30 min;显色:用洗涤液洗板5次,依次加入显色剂A和显色剂B 50 μL,37 ℃避光反应10 min;终止:加入终止液50 μL。最后以空白孔调零,450 nm波长处测定各孔的吸光度。以标准品浓度为横坐标,吸光度为纵坐标,绘制标准曲线y=0.029x-0.0161,R²=0.997,标准品在0~60 ng/L范围内线性良好。
1.3 数据处理
所有试验均重复测定三次或以上,使用Microsoft Office Excel 2010软件进行绘图,采用SPSS 27软件进行统计分析,P<0.05代表差异显著,试验结果表示为平均值±标准差。
2. 结果与分析
2.1 均方根偏差分析
通过计算黄芩素周围20 Å范围内残基的均方根偏差(root mean square deviation,RMSD)值,可以考察体系在150 ns 分子动力学模拟过程中的稳定性。对于Dimer体系,选择与复合物体系相同的残基并计算其RMSD值。由图2可知,两个体系的RMSD值变化情况有所不同,复合物体系在3 ns内急速上升,之后波动幅度较小,随着模拟时间的延长,稳定在2.66 Å左右。Dimer体系在5 ns时突增至3.07 Å,5~30 ns波动在3.50 Å左右,但30 ns后,RMSD波动幅度较大,甚至高达5.35 Å,60 ns后RMSD值基本收敛至3.11 Å。说明复合物比Dimer体系具有更高的结构稳定性。综上,两个体系均达到了平衡,可用于后续分析。
2.2 均方根波动分析
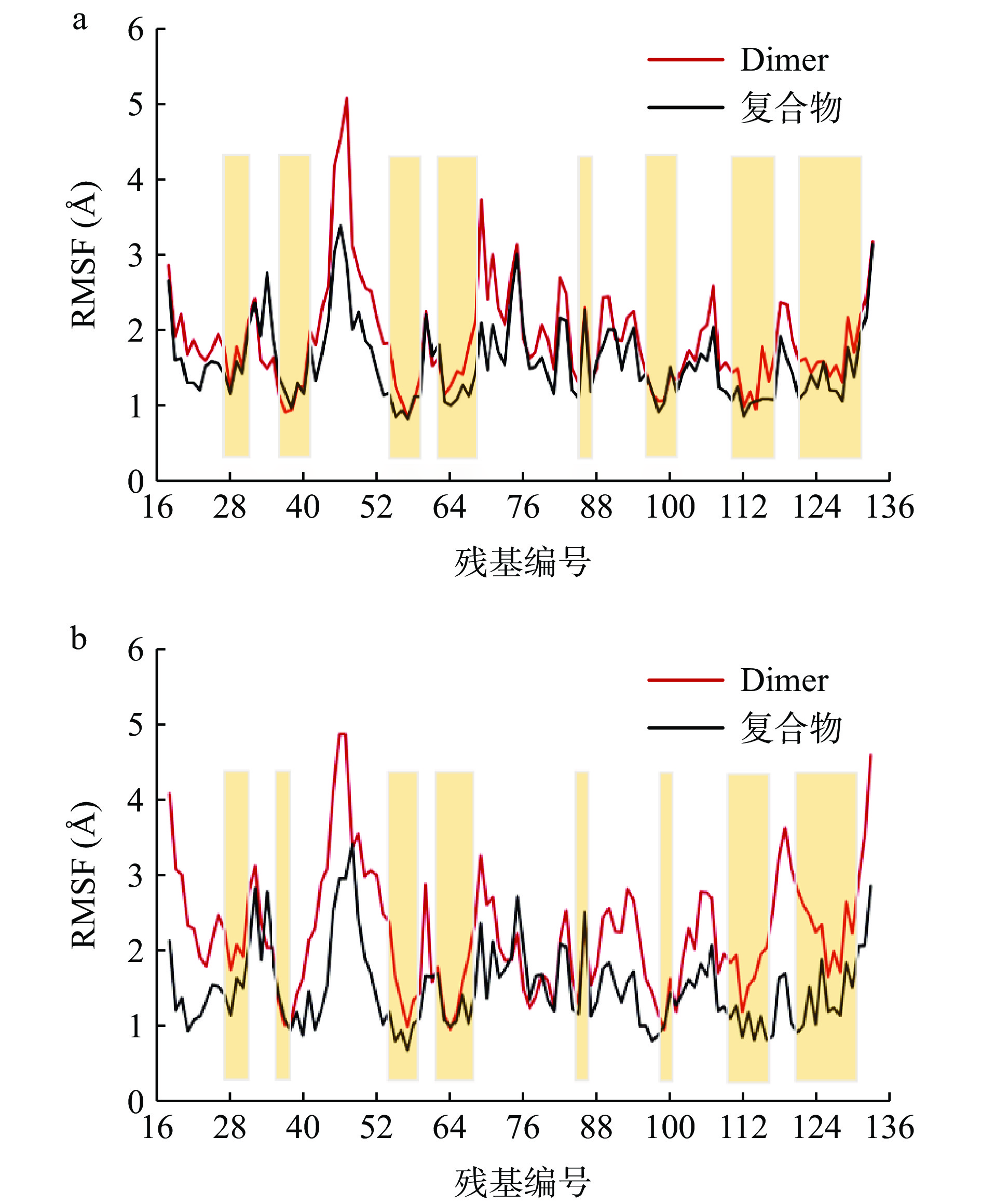
为了比较复合物和Dimer体系在模拟过程中构象柔性的差异,计算了PD-L1 dimer残基的均方根波动(root mean square fluctuation,RMSF)值,结果见图3。整体来看,除少数区域外,两个体系RMSF的趋势较为相似,但复合物比Dimer体系具有更低的柔性。进一步观察发现波动较大的残基主要位于两个体系的N端、C端和loop区,其中Dimer体系BC loop区残基RMSF值达到了5 Å。复合物体系结构柔性显著较低的区域主要集中于β折叠结构域,其RMSF值仅为1~3 Å,如C-sheet(残基54~59)、F-sheet(残基121~124)和G-sheet(残基110~117)。综上,黄芩素的结合主要降低了sheet区域的柔性,重要的是该区域为PD-1与PD-L1的主要结合位点,这与以往的研究结果相似[7−8,15−16,18]。
2.3 结合自由能分析
抑制剂与蛋白的结合自由能可用于描述两者间结合亲和力的强弱[26]。为了评估这一特性,本文利用g_mmpbsa程序计算了黄芩素与PD-L1 dimer的结合自由能,并详细解析了相互作用成分的能量贡献。由表1可知,黄芩素与PD-L1 dimer的ΔG为−32.41±0.31 kcal/mol,说明两者具有较强的结合亲和力。相比之下,Dimer体系的ΔG为正值(36.11±0.89 kcal/mol),说明黄芩素是PD-L1 dimer稳定存在的必备条件。根据MM-PBSA方法,ΔG可表示为总极性能(ΔEpolar,total)和总非极性能(ΔEnonpolar,total)之和,两者可进一步分解为ΔEele+ΔEPB和ΔEvdw+ΔESA。复合物体系的ΔEvdw和ΔESA分别为−45.61±0.19和−3.41±0.03 kcal/mol,说明两者均有利于黄芩素的结合。ΔEele也提供了−2.61±0.47 kcal/mol的有利贡献,但完全被不利于黄芩素结合的极性溶解自由能(19.22±0.60 kcal/mol)抵消,产生了不利于结合的总极性相互作用(16.61±1.07 kcal/mol)。综上所述,总非极性相互作用是黄芩素与PD-L1 dimer结合的主要驱动力,而总极性作用不利于结合,这类似于本人前期关于天然小分子抑制PD-1/PD-L1相互作用的研究[23]。此外,黄芩素抑制该通路的能力近似于姜黄素,但强于白藜芦醇和表没食子儿茶素没食子酸酯[23]。
表 1 复合物和Dimer体系的结合自由能(kcal/mol)Table 1. Binding free energies of the complex and Dimer systems (kcal/mol)相互作用能 复合物 Dimer ΔEvdwa −45.61±0.19 −44.59±9.85 ΔEeleb −2.61±0.47 −124.35±23.36 ΔEPBc 19.22±0.60 211.28±17.07 ΔESAd −3.41±0.03 −6.23±0.37 ΔEpolar,totale 16.61±1.07 86.94±10.00 ΔEnonpolar,totalf −49.02±0.22 −50.82±10.06 ΔGg −32.41±0.31 36.11±0.89 注:a:范德华相互作用能;b:静电相互作用能;c:极性溶剂化能;d:非极性溶剂化能;e:总极性能;f:总非极性能;g:结合自由能;从120~150 ns提取300帧构象用于计算结合自由能的平均值。 2.4 结合能分解
使用MM-PBSA方法对总结合自由能进行分解以识别对黄芩素结合有重要作用的残基,结果见图4。黄芩素与PD-L1 dimer的6个残基产生了强于−1 kcal/mol的相互作用,分别是ATyr56、AMet115、AAla121、BMet115、BAla121和BAsp122。在这些残基中,AMet115与黄芩素的相互作用最强,作用能为−2.34 kcal/mol;ATyr56次之,结合自由能贡献为−1.49 kcal/mol;BAsp122的贡献最小,为−1.03 kcal/mol。此外,其他残基如AIle54和AIle116对黄芩素的结合也起到了一定的作用,两者的贡献分别为−0.91和−0.90 kcal/mol。综上所述,Tyr56、Met115、Ala121和Asp122为复合物体系的关键残基。本人前期的研究表明Tyr56和Met115为天然小分子姜黄素、白藜芦醇和表没食子儿茶素没食子酸酯的关键结合残基。类似地,Zak等[7]和Ahmed等[27]的研究表明,残基Met115和Tyr56侧链结构重排有利于合成小分子结合。重要的是这些关键残基也参与了PD-L1/PD-1相互作用。综上,从能量方面看,黄芩素可直接与PD-L1 dimer稳定结合。
2.5 接触数分析
为了确定黄芩素结合区域,计算了复合物体系的分子间接触数,并将与黄芩素接触数大于10的残基视为重要残基[28]。由图5可知,黄芩素主要结合在PD-L1 dimer的4个区域,分别为C-sheet(残基54~56)、C'-sheet(残基66~68)、F-sheet(残基115~117)和G-sheet(残基121~124)。其中,C-sheet的残基Ile54和Tyr56与黄芩素有很大的接触数分布,Val55与黄芩素的接触稍弱,但AVal55的接触数大于10。因此这三个残基为该区域的重要残基。C'-sheet三个残基与黄芩素的接触较弱,其中极性残基AGln66与黄芩素之间的接触数最大,这主要来源于氢键的贡献(图6)。F-sheet残基与黄芩素的接触数分布较大,其中非极性残基AMet115与黄芩素的接触数为34。G-sheet非极性残基AAla121、BAla121和极性残基BAsp122分别贡献了30、36和23的接触数,这与结合能分解结果一致。表2为黄芩素与结合区域的接触数。由表可知,复合物体系接触数总和为389,这与姜黄素的相关结果类似[23]。此外,黄芩素与各结合区域的接触数呈G-sheet>F-sheet>C-sheet>C'-sheet趋势,说明黄芩素与G-sheet的结合最强,而与C'-sheet的结合最弱。
表 2 黄芩素与结合区域的接触数Table 2. Contact numbers between baicalein and the binding domains名称 C-sheet C'-sheet F-sheet G-sheet Sheet 黄芩素 90 20 133 146 389 2.6 非键相互作用分析
基于黄芩素的结构,猜测其与PD-L1 dimer之间的相互作用类型主要为氢键和疏水相互作用。因此首先对复合物体系分子间氢键占有率进行了定量分析。如表3所示,黄芩素O2和O3原子分别与残基AVal55和AGln66形成占有率为15.28%和10.30%的氢键。表明氢键在模拟过程中不稳定,这与静电相互作用能结果一致(−2.61 kcal/mol)。然后对复合物体系的结合模式进行了评价。如图6所示,黄芩素位于APD-L1和BPD-L1之间圆柱形结合口袋中,且被残基BIle54、AMet115、AAla121、BMet115、BAla121、ATyr56、BAsp122、AVal55和AGln66的侧链包围,其中前5个残基与黄芩素形成了紧密的疏水相互作用。这与结合能分解结果一致地表明,残基Tyr56、Met115、Ala121和Asp122可能是PD-1/PD-L1通路天然的小分子抑制剂的潜在靶点。此外,相比于氢键,黄芩素的结合更依赖于苯环与疏水残基之间的疏水相互作用。
表 3 复合物体系的氢键占有率Table 3. Hydrogen bond occupancies of the complex system供体 氢供体 受体 占有率(%) 黄芩素@O2 H2 AVal55@N 15.28 黄芩素@O3 H3 AGln66@OE1 10.30 2.7 互相关矩阵分析
为了探究黄芩素对PD-L1 dimer原子运动性的影响,计算了残基Cα原子的互相关矩阵[29]。矩阵中对角线颜色表示残基的运动程度,对角线外红色部分(正值)代表残基间运动呈正相关,即残基间的动力学运动方向一致。而蓝色部分(负值)代表残基间的运动有负相关性,即残基间的动力学运动方向相反[30]。如图7所示,对角线尤其是残基132~143和242~250(分别对应于APD-L1的132-143和BPD-L1的132-141)颜色偏红,说明两个体系C端残基均具有较高的灵活性。此外,复合物体系蓝色区域较少,而Dimer体系蓝色区域占据了矩阵大部分面积,说明该体系中APD-L1和BPD-L1之间残基运动具有更强的负相关性。综上,黄芩素可稳定PD-L1 dimer的结构。
2.8 二级结构分析
利用DSSP程序计算了黄芩素和Dimer体系蛋白二级结构随时间的变化规律。如图8所示,Dimer体系的β-折叠,如残基37~42、93~100和104~114等(分别对应于APD-L1的残基54~59、110~117和121~123)稳定存在于整个动力学模拟过程。残基32~35(APD-L1的残基49~52)主要在3-螺旋和转角之间相互转变,其中3-螺旋出现的更频繁,而残基158~161(BPD-L1的残基49~52)表现出相反的动力学行为;残基72~77和198~204(分别对应于APD-L1的残基89~94和BPD-L1的残基89~95)的二级结构包括3-螺旋、α-螺旋和转角;残基116~126(APD-L1的残基133~143)的二级结构在前84 ns表现为α-螺旋,之后转变为转角、3-螺旋和无规则卷曲;残基242~249(BPD-L1的残基133~140)也包括这些二级结构,但这些构象时而出现时而消失,表明PD-L1 dimer的C端不稳定。复合物体系二级结构的组成类似于Dimer体系,整个模拟过程中β-折叠构象一直保持稳定,其中C-sheet、F-sheet和G-sheet是PD-1与PD-L1的关键结合区域。因此可以推断黄芩素能与PD-L1 dimer稳定结合从而抑制PD-1/PD-L1相互作用。
2.9 PD-1/PD-L1相互作用抑制率
为了阐明黄芩素对PD-1/PD-L1相互作用的抑制能力,以BMS-202为阳性对照进行了ELISA试验,结果见图9。由图9可知,随着BMS-202和黄芩素浓度的增加,两者对PD-1/PD-L1相互作用的抑制率呈显著升高趋势(P<0.05),且BMS-202的抑制率始终大于黄芩素。当浓度为6.25 µg/L时,黄芩素对PD-1/PD-L1通路的抑制率(17.95%±0.92%)与BMS-202的抑制率(19.69%±0.85%)差异不显著(P>0.05)。当浓度为50 µg/L时,黄芩素与BMS-202的抑制率分别达到43.43%和52.06%,差异显著(P<0.05)。黄芩素与BMS-202对PD-1/PD-L1相互作用抑制率的IC50分别为79.47和44.29 µg/L,表明黄芩素对该通路较强的抑制作用[31−32]。
3. 结论
本文利用分子动力学模拟和实验验证研究了黄芩素抑制PD-1/PD-L1相互作用的分子机制。构象动力学结果表明,PD-L1 dimer与黄芩素的结合在整个模拟过程中基本保持稳定;结合自由能结果表明,黄芩素稳定PD-L1 dimer的能力较强为−32.41±0.31 kcal/mol;通过对结合能进行分解,发现PD-L1 dimer的4个关键残基Tyr56、Metl15、Ala121和Asp122对黄芩素结合有重要贡献;结合模式和相互作用结果表明黄芩素主要结合在PD-L1 dimer的C-sheet、F-sheet和G-sheet区域,其中苯环与关键残基间的非极性相互作用是复合物稳定的主要因素;互相关矩阵和二级结构结果进一步表明,黄芩素可稳定结合在sheet区域。ELISA结果表明黄芩素是PD-1/PD-L1相互作用的有效阻断剂。总之,这些信息有助于筛选PD-1/PD-L1通路天然小分子抑制剂。
-
表 1 复合物和Dimer体系的结合自由能(kcal/mol)
Table 1 Binding free energies of the complex and Dimer systems (kcal/mol)
相互作用能 复合物 Dimer ΔEvdwa −45.61±0.19 −44.59±9.85 ΔEeleb −2.61±0.47 −124.35±23.36 ΔEPBc 19.22±0.60 211.28±17.07 ΔESAd −3.41±0.03 −6.23±0.37 ΔEpolar,totale 16.61±1.07 86.94±10.00 ΔEnonpolar,totalf −49.02±0.22 −50.82±10.06 ΔGg −32.41±0.31 36.11±0.89 注:a:范德华相互作用能;b:静电相互作用能;c:极性溶剂化能;d:非极性溶剂化能;e:总极性能;f:总非极性能;g:结合自由能;从120~150 ns提取300帧构象用于计算结合自由能的平均值。 表 2 黄芩素与结合区域的接触数
Table 2 Contact numbers between baicalein and the binding domains
名称 C-sheet C'-sheet F-sheet G-sheet Sheet 黄芩素 90 20 133 146 389 表 3 复合物体系的氢键占有率
Table 3 Hydrogen bond occupancies of the complex system
供体 氢供体 受体 占有率(%) 黄芩素@O2 H2 AVal55@N 15.28 黄芩素@O3 H3 AGln66@OE1 10.30 -
[1] 岳露, 金双龙, 高健, 等. 联苯类PD-L1抑制剂的设计合成及生物活性评价[J]. 中国药物化学杂志,2019,29(6):417−425. [YUE L, JIN S L, GAO J, et al. Design, synthesis and biological evaluation of diphenyl-based PD-L1 inhibitors[J]. Chinese Journal of Medicinal Chemistry,2019,29(6):417−425. YUE L, JIN S L, GAO J, et al . Design, synthesis and biological evaluation of diphenyl-based PD-L1 inhibitors[J]. Chinese Journal of Medicinal Chemistry,2019 ,29 (6 ):417 −425 .[2] WU Q, JIANG L, LI S, et al. Small molecule inhibitors targeting the PD-1/PD-L1 signaling pathway[J]. Acta Pharmacologica Sinica,2021,42(1):1−9. doi: 10.1038/s41401-020-0366-x
[3] 张昕彤, 王坤, 曾庆轩, 等. 基于PD-L1肿瘤免疫苦豆碱类衍生物的合成与活性研究[J]. 药学学报,2022,57(4):1085−1094. [ZHANG, X T, WANG K, ZENG Q X, et al. Synthesis and activity evaluation of aloperine derivatives based on PD-L1 tumor immunity[J]. Acta Pharmaceutica Sinica,2022,57(4):1085−1094. ZHANG, X T, WANG K, ZENG Q X, et al . Synthesis and activity evaluation of aloperine derivatives based on PD-L1 tumor immunity[J]. Acta Pharmaceutica Sinica,2022 ,57 (4 ):1085 −1094 .[4] RI M H, MA J, JIN X. Development of natural products for anti-PD-1/PD-L1 immunotherapy against cancer[J]. Journal of Ethnopharmacology,2021,281:114370. doi: 10.1016/j.jep.2021.114370
[5] NAIDOO J, PAGE D B, LI B T, et al. Toxicities of the anti-PD-1 and anti-PD-L1 immune checkpoint antibodies[J]. Annals of Oncology,2015,26(12):2375−2391. doi: 10.1093/annonc/mdv383
[6] SANGRO B, CHAN S L, MEYER T, et al. Diagnosis and management of toxicities of immune checkpoint inhibitors in hepatocellular carcinoma[J]. Journal of Hepatology,2020,72(2):320−341. doi: 10.1016/j.jhep.2019.10.021
[7] ZAK K M, GRUDNIK P, GUZIK K, et al. Structural basis for small molecule targeting of the programmed death ligand 1 (PD-L1)[J]. Oncotarget,2016,7(21):30323. doi: 10.18632/oncotarget.8730
[8] SKALNIAK L, ZAK K M, GUZIK K, et al. Small-molecule inhibitors of PD-1/PD-L1 immune checkpoint alleviate the PD-L1-induced exhaustion of T-cells[J]. Oncotarget,2017,8(42):72167. doi: 10.18632/oncotarget.20050
[9] 王岱东, 屠鹏飞, 黄亚卓, 等. 人参中PD-1小分子抑制剂的筛选及活性验证[J]. 药学学报,2020,55(10):2428−2434. [WANG D D, TU P F, HUANG Y A, et al. Identification of PD-1 small molecule inhibitors and validation in Panax ginseng[J]. Acta Pharmaceutica Sinica,2020,55(10):2428−2434. WANG D D, TU P F, HUANG Y A, et al . Identification of PD-1 small molecule inhibitors and validation in Panax ginseng[J]. Acta Pharmaceutica Sinica,2020 ,55 (10 ):2428 −2434 .[10] KE M, ZHANG Z, XU B, et al. Baicalein and baicalin promote antitumor immunity by suppressing PD-L1 expression in hepatocellular carcinoma cells[J]. International Immunopharmacology,2019,75:105824. doi: 10.1016/j.intimp.2019.105824
[11] SONG L, ZHU S, LIU C, et al. Baicalin triggers apoptosis, inhibits migration, and enhances anti‐tumor immunity in colorectal cancer via TLR4/NF- κB signaling pathway[J]. Journal of Food Biochemistry,2022,46(3):e13703.
[12] 郑敦锦, 沈锐锋, 何康平, 等. 分子动力学模拟与热稳定性实验相结合分析乙酰氨基葡萄糖与脂肪酶的相互作用机制[J]. 现代食品科技,2022,38(3):74−81. [ZHENG D J, SHEN R F, HE K P, et al. Molecular dynamics simulation combined with thermal stability experiments to analyze the interaction mechanism between acetylglucosamine and lipase[J]. Modern Food Science and Technology,2022,38(3):74−81. ZHENG D J, SHEN R F, HE K P, et al . Molecular dynamics simulation combined with thermal stability experiments to analyze the interaction mechanism between acetylglucosamine and lipase[J]. Modern Food Science and Technology,2022 ,38 (3 ):74 −81 .[13] SUN X, YAN X, ZHUO W, et al. PD-L1 nanobody competitively inhibits the formation of the PD-1/PD-L1 complex:Comparative molecular dynamics simulations[J]. International Journal of Molecular Sciences,2018,19(7):1984. doi: 10.3390/ijms19071984
[14] SHI D, ZHOU S, LIU X, et al. Understanding the structural and energetic basis of PD-1 and monoclonal antibodies bound to PD-L1:A molecular modeling perspective[J]. Biochimica et Biophysica Acta (BBA)-General Subjects,2018,1862(3):576−588. doi: 10.1016/j.bbagen.2017.11.022
[15] VERDURA S, CUYAS E, CORTADA E, et al. Resveratrol targets PD-L1 glycosylation and dimerization to enhance antitumor T-cell immunity[J]. Aging,2020,12(1):8. doi: 10.18632/aging.102646
[16] GUO Y, JIN Y, WANG B, et al. Molecular mechanism of small-molecule inhibitors in blocking the PD-1/PD-L1 pathway through PD-L1 dimerization[J]. International Journal of Molecular Sciences,2021,22(9):4766. doi: 10.3390/ijms22094766
[17] WU X, WANG N, LIANG J, et al. Is the triggering of PD-L1 dimerization a potential mechanism for food-derived small molecules in cancer immunotherapy? A study by molecular dynamics[J]. International Journal of Molecular Sciences,2023,24:1413. doi: 10.3390/ijms24021413
[18] LIANG J, WANG B, YANG Y, et al. Approaching the dimerization mechanism of small molecule inhibitors targeting PD-L1 with molecular simulation[J]. International Journal of Molecular Sciences 2023, 24, 1280.
[19] 都宵晓, 孟凡翠, 刘巍, 等. 胰高血糖素样肽-1受体的分子动力学模拟研究[J]. 中国新药杂志,2021,30(8):732−739. [DU X X, MENG F C, LIU L, et al. Molecular dynamics simulation study of glucagon-like peptide-1 receptor[J]. Chinese Journal of New Drugs,2021,30(8):732−739. DU X X, MENG F C, LIU L, et al . Molecular dynamics simulation study of glucagon-like peptide-1 receptor[J]. Chinese Journal of New Drugs,2021 ,30 (8 ):732 −739 .[20] HORNAK V, ABEL R, OKUR A, et al. Comparison of multiple Amber force fields and development of improved protein backbone parameters[J]. Proteins:Structure, Function, and Bioinformatics, 2006, 65(3):712-725.
[21] WANG J, WOLF R M, CALDWELL J W, et al. Development and testing of a general Amber force field[J]. Journal of Computational Chemistry,2004,25(9):1157−1174. doi: 10.1002/jcc.20035
[22] GENHEDEN S, RYDE U. The MM/PBSA and MM/GBSA methods to estimate ligand-binding affinities[J]. Expert Opinion on Drug Discovery,2015,10(5):449−461. doi: 10.1517/17460441.2015.1032936
[23] GUO Y, LIANG J, LIU B, et al. Molecular mechanism of food-derived polyphenols on PD-L1 dimerization:A molecular dynamics simulation study[J]. International Journal of Molecular Sciences,2021,22(20):10924. doi: 10.3390/ijms222010924
[24] WANG Q, NING L, NIU Y, et al. Molecular mechanism of the inhibition and remodeling of human islet amyloid polypeptide (hIAPP1–37) oligomer by resveratrol from molecular dynamics simulation[J]. The Journal of Physical Chemistry B,2015,119(1):15−24. doi: 10.1021/jp507529f
[25] DRAGIC T, TRKOLA A, THOMPSON D A D, et al. A binding pocket for a small molecule inhibitor of HIV-1 entry within the transmembrane helices of CCR5[J]. Proceedings of the National Academy of Sciences,2000,97(10):5639−5644. doi: 10.1073/pnas.090576697
[26] 桑鹏, 李智, 杨力权, 等. 基于分子动力学模拟和自由能计算的非小细胞肺癌对克唑替尼(crizotinib)耐药性研究[J]. 云南大学学报(自然科学版),2020,42(4):760−767. [SANG P, LI Z, YANG L Q, et al. Insight into crizotinib resistance of non-small cell lung cancer derived from molecular dynamics simulations and free energy analysis[J]. Journal of Yunnan University: Natural Sciences Edition,2020,42(4):760−767. SANG P, LI Z, YANG L Q, et al . Insight into crizotinib resistance of non-small cell lung cancer derived from molecular dynamics simulations and free energy analysis[J]. Journal of Yunnan University: Natural Sciences Edition,2020 ,42 (4 ):760 −767 .[27] AHMED M, BARAKAT K. The too many faces of PD-L1:A comprehensive conformational analysis study[J]. Biochemistry,2017,56(40):5428−5439. doi: 10.1021/acs.biochem.7b00655
[28] GUO J, SUN W, LI L, et al. Brazilin inhibits fibrillogenesis of human islet amyloid polypeptide, disassembles mature fibrils, and alleviates cytotoxicity[J]. RSC Advances,2017,7(69):43491−43501. doi: 10.1039/C7RA05742C
[29] ZHAN D, GUAN S, JIN H, et al. Stereoselectivity of phosphotriesterase with paraoxon derivatives:A computational study[J]. Journal of Biomolecular Structure and Dynamics,2016,34(3):600−611. doi: 10.1080/07391102.2015.1046937
[30] GUAN S, WANG T, KUAI Z, et al. Exploration of binding and inhibition mechanism of a small molecule inhibitor of influenza virus H1N1 hemagglutinin by molecular dynamics simulation[J]. Scientific Reports,2017,7(1):3786. doi: 10.1038/s41598-017-03719-4
[31] KIM J H, KIM Y S, CHOI J G, et al. Kaempferol and its glycoside, kaempferol 7-O-rhamnoside, inhibit PD-1/PD-L1 interaction in vitro[J]. International Journal of Molecular Sciences,2020,21(9):3239. doi: 10.3390/ijms21093239
[32] LI W, KIM T I, KIM J H, et al. Immune checkpoint PD-1/PD-L1 CTLA-4/CD80 are blocked by Rhus verniciflua stokes and its active compounds[J]. Molecules,2019,24(22):4062. doi: 10.3390/molecules24224062
-
期刊类型引用(5)
1. 高含,刘锐,姜铖,王飞飞. 超高效液相色谱—串联质谱法测定植物油中甲胺磷残留量的不确定度评定. 食品与机械. 2024(10): 62-67 .  百度学术
百度学术
2. 董孝元,周玉,余义,刘莎,汪明迪,孙莉,唐艳荣. LC-ESI-MS/MS测定白酒中氨基甲酸乙酯的方法研究. 酿酒科技. 2023(11): 105-111 .  百度学术
百度学术
3. 聂叶,焦富,罗汝叶,李巧玉,牟明月. 酱香型白酒酒醅中乙醇测定方法的不确定度评定. 酿酒科技. 2022(08): 125-130 .  百度学术
百度学术
4. 陈同强,梁锋,吴海智,向俊,宋阳,荆辉华,袁列江,李灿,李凯龙. 气相色谱-质谱法测定发酵乳中氨基甲酸乙酯含量. 乳业科学与技术. 2022(06): 18-21 .  百度学术
百度学术
5. 李正刚,马彧,王丹彧,李本淳,赵艳. HPLC法测定制何首乌饮片中2, 3, 5, 4'-四羟基二苯乙烯-2-O-β-D-葡萄糖苷含量的不确定度评估. 中国医药导刊. 2021(07): 522-525 .  百度学术
百度学术
其他类型引用(0)





 下载:
下载:






 下载:
下载:



