Detection of Pork-Derived Ingredients Based on Real-time Quantitative PCR
-
摘要: 为了准确可靠地对肉制品中猪源性成分进行定量检测,通过生物信息学方法筛选到猪细胞核单拷贝基因(carcinoembryonic antigen-related cell adhesion molecule 2-like,CACA)。以CACA基因为扩增靶标,设计了特异性引物、TaqMan探针,建立了基于实时荧光定量PCR技术检测猪肉含量的方法。实验结果表明,该方法具有良好的种外特异性和种内稳定性,在20~0.032 ng/µL的DNA浓度范围内,模板DNA和扩增Ct值之间存在良好的线性关系,标准曲线为y=−3.508x+28.636,线性决定系数R2为0.997。在相对标准偏差≤25%的条件下,可准确检测猪DNA含量低至0.1%的DNA样品,猪肉含量低至5.0%的肉制品。通过对市售样品的检测,发现有的肉制品中掺有猪肉但未标识,有的配料表中猪肉并非主要成分但实际上猪肉占主要成分。本研究建立的实时荧光定量PCR能够准确可靠对肉制品中的猪肉成分进行检测,对准确鉴别肉制品掺假以及量化肉制品组分具有重要参考价值。Abstract: In order to accurately and reliably quantify pork-derived ingredients in meat products, single-copy gene (carcinoembryonic antigen-related cell adhesion molecule 2-like, CACA) in pig cell nucleus was screened by bioinformatics methods, with CACA gene as the amplification target, specific primers and TaqMan probes were designed, and a TaqMan real-time quantitative PCR method for detecting pork ingredients was established. The experimental results showed that the method had good extraspecies specificity and intraspecies stability. There was a good linear relationship between the template DNA and the amplified Ct value within the DNA concentration range from 20 to 0.032 ng/µL. The standard curve was y=−3.508x+28.636, the coefficient of determination (R2) value was 0.997. Under the condition of relative standard deviation ≤25%, it could accurately detect DNA samples with pork DNA content as low as 0.1%, and meat products with pork content as low as 5.0%. Through testing of commercially available samples, it was found that somemeat products were mixed with pork but were not labeled. And some meat products, pork was not listed as the main ingredient but in fact pork was the main ingredient. The real-time quantitative PCR method established in this study could be used to accurately and reliably detect pork ingredients in meat products. It has important reference value for accurately identifying adulteration of meat products and quantifying the ingredients of meat products.
-
近年来,肉制品掺假事件的相关报道频频出现,例如2013年欧洲的“马肉风波”[1]、国内市场的“老鼠肉、狐狸肉和水貂肉冒充牛羊肉”、“鸭肉制牛羊肉卷”等事件[2]。虽然国内外政府部门都明文规定食品制造商应当在食品包装上标注配料种类及含量[3],但仍有许多不法商贩为了赚取高额利润,以价格低廉的鸭肉、鸡肉、猪肉、水貂肉及其他动物肉冒充价格较高的羊肉、牛肉[4]。特别是在牛、羊肉中掺入猪肉,既损害了消费者的利益,影响了肉制品贸易的公平性,还触犯了宗教中的饮食禁忌[5]。
近几十年来,以核酸为标志物的肉制品鉴别检测方法飞速进步,并获得了广泛应用[5-7]。在GB/T 35917-2018常见动物源性成分快速测定中,利用线粒体ATPase 6, cox1, cytb, D-loop等基因序列对肉制品及饲料中猪、黄牛、羊、鸡、兔、驴、貂、狐、鼠、牦牛、鸭,共11种常见动物源性成分进行快速检测[8]。CAMMA等[9]利用cytb和16S rRNA对火鸡、鸡、牛、猪、羊进行鉴别。SAFDAR等[10]建立了基于cytb和12S rRNA基因的SYBRGreen二重荧光定量PCR方法,可同时检测肉制品中牛源性和鸡源性成分。KIM等[11]建立了基于D-loop基因的Taq-man荧光定量PCR方法对猪源性成分进行检测。HAIDER等[12]建立了基于COI基因的PCR-RFLP检测方法。线粒体DNA在细胞内有较多的拷贝数,cyt-b、12S rRNA、16S rRNA、D-loop、COI等基因均位于线粒体基因组上,以线粒体基因为检测靶标有助于提高检测的灵敏度[13]。但是由于线粒体DNA拷贝数在相同组织的不同时期,以及不同组织如肌肉、内脏中差异显著[14],基于线粒体DNA的检测方法仅适用于定性分析[15-16]。
细胞核单拷贝基因在动物不同时期、组织中都具有较为稳定的拷贝数,近年来物种特异的单拷贝靶序列成为动物源成分定量检测的热点[17-18]。基于细胞核单拷贝基因的实时荧光定量检测方法具有特异性强、灵敏度高、结果较为准确等优点,亟需针对各种动物筛选具有物种特异性的细胞核单拷贝基因[19-20]。本研究通过生物信息学和分子生物学手段筛选和分离猪(Susscrofa)细胞核基因组中特异性的单拷贝基因,设计猪特异性扩增引物与探针,建立Taq-man实时荧光定量PCR方法,考察其在不同物种间的特异性、在猪不同品种间的稳定性,以及检测的灵敏度。并对已知猪DNA含量的混合DNA样品和已知猪肉含量的混合肉样进行定量检测,考察检测方法的适用性。为肉制品中猪源性成分的定性检测和定量分析提供方法参考,为肉制品贸易的监督和管理提供技术支持。
1. 材料与方法
1.1 材料与仪器
6个不同品种猪肉(恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪)、13种动物(鸡、鸭、鹅、牛、驴、羊、狗、鱼、鱿鱼、虾、扇贝、骆驼、小鼠)、5种植物(大豆、小麦、玉米、拟南芥、烟草) 为本实验室收集并保存,材料详细信息如表1所示;菜场牛肉丸、鱼丸、超市品牌牛肉丸、品牌羊肉卷、品牌肥羊卷、品牌肥牛卷、品牌牛排等肉制品 市售;Hieff PCR Master mix(货号10102ES03)、HieffTMqPCR SYBR Green Master Mix(货号11201ES08)、HieffTM qPCR TaqMan Probe Master Mix(货号11205ES08) 上海翊圣生物技术有限公司;DNA小量提取试剂盒DNeasy Plant Mini Kit(货号69104) Qiagen公司;PCR引物 上海生物工程技术服务有限公司。
表 1 特异性验证实验中所用到的材料的详细信息Table 1. Detailed information about the materials used in species specificity analysis样品编号 种类 通用名 学名 1 家禽 鸡 Gallus gallus 2 鸭 Anas platyrhynchos 3 鹅 Anser domestica 4 家畜 牛 Bos taurus 5 驴 Equus asinus 6 绵羊 Ovis aries 7 猪 Sus scrofa 8 狗 Canis lupus familiaris 9 水产品 草鱼 Ctenopharyngodon idella 10 鱿鱼 Illex argentines 11 虾 Penaeus orientalis 12 扇贝 Patinopecten yessoensis 13 模式动物 小鼠 Mus musculus 14 其他动物 骆驼 Camelus bactrianus 15 植物 大豆 Glycine max 16 小麦 Triticum aestivum 17 玉米 Zea mays 18 拟南芥 Arabidopsis thaliana 19 烟草 Nicotiana tabacum NanoPhotometer NP80超微量紫外分光光度计 Implen公司;C1000 Touch Thermal Cycler定性PCR仪、CFX96定量PCR仪 Bio-Rad公司;UVCI-1100凝胶成像系统 Major science公司;5424小型离心机 Eppendorf公司;ME303分析天平 梅特勒-托利多公司;DHG-9240A鼓风干燥箱 上海精宏实验设备有限公司;JYL-G12绞肉机 九阳股份有限公司。
1.2 实验方法
1.2.1 样品前处理
采集不同动物的新鲜肌肉组织,家禽采集胸部肌肉,家畜、小鼠、骆驼、草鱼采集脊柱背侧肌肉,鱿鱼采集外套膜肌肉、虾采集腹部肌肉,扇贝采集闭壳肌,剔除样品中的肌腱和脂肪,用组织绞肉机绞碎后,置于60 ℃鼓风干燥箱中烘约72 h。烘干的样品粉末放入灭菌洁净的研钵中,加入液氮迅速研磨成细小的粉末备用。处理过程中不同肉类要分开,以防止不同来源的动物组织交叉污染。
1.2.2 基因组DNA的提取与检测
称取12 mg液氮研磨后的鲜肉粉末置于2.0 mL灭菌离心管中,按照汪永庆等[21]的方法提取动物基因组DNA。按照植物DNA提取试剂盒DNeasy Plant Mini Kit的说明书提取植物叶片基因组DNA。使用超微量紫外分光光度计测定提取后的基因组DNA浓度与纯度,用于实验的基因组DNA样品OD260/280值应在1.80左右。使用真核生物
18S rDNA基因引物[22](表2)对提取的基因组DNA进行SYBR Green I实时荧光定量PCR扩增(反应程序与体系见1.2.5),判断基因组DNA的可扩增性。 表 2 引物和探针的序列Table 2. Primer and probe sequences引物和探针 序列(5’-3’) 靶基因 18S-EUKF AGCCTGCGGCTTAATTTGAC 18S rDNA 18S-EUKR CAACTAAGAACGGCCATGCA CACAF21 CAGCCACTTCCCAGGATACC CACA CACAR162 CCACTGTCCAACACTCGCAC CACAP69 FAM-ACGCCCTCACTCCAGAACCAGCC-BHQ1 1.2.3 猪特异性基因的获取
根据GenBank中猪(Susscrofa)全基因组序列信息(ID: 84),利用生物信息学方法进行全基因组自我比对,只能对本序列匹配的基因,可判定为单拷贝基因。然后将候选的单拷贝基因在NCBI中进行Blastn分析,筛选出特异强、同源序列少的基因序列。以这些基因序列为基础,设计PCR引物,并对PCR扩增片段进行再次Blastn分析,以保证扩增片段的特异性。
1.2.4 定性PCR扩增和检测
定性PCR反应体系为:20 ng/µL的DNA 模板2 μL,Hieff PCR Master mix 25 μL,10 μmol/L正、反向引物各0.8 μL,ddH2O补足至50 μL。定性PCR反应条件为:94 ℃预变性5 min;95 ℃变性30 s,60 ℃退火30 s,72 ℃延伸30 s,35个循环;72 ℃延伸10 min。PCR产物用1.5%琼脂糖凝胶进行电泳,电泳后用凝胶成像系统进行检测。PCR产物送至武汉擎科生物科技有限公司进行测序。
1.2.5 荧光定量PCR反应体系与程序
SYBR Green Ⅰ实时荧光定量PCR反应体系为:DNA模板2 μL,Hieff qPCR SYBR Green Master Mix 10 μL,10 μmol/L正、反向引物各0.4 μL,ddH2O补足至20 μL。SYBR Green Ⅰ实时荧光定量PCR反应条件为:95 ℃预变性5 min;95 ℃变性10 s,60 ℃退火和延伸30 s,40个循环;熔点曲线:65~95 ℃每隔0.5 ℃读板一次,16 ℃保温。
实时荧光定量PCR(TaqMan)反应体系为:DNA 模板2 μL,Hieff qPCR TaqMan Probe Master Mix 10 μL,10 μmol/L正、反向引物各0.4 μL,10 μmol/L探针0.2 μL,ddH2O补足至20 μL。TaqMan实时荧光定量PCR反应条件为:95 ℃预变性2 min;95 ℃变性10 s,60 ℃退火和延伸1 min,40个循环。所有PCR反应设置3个平行。
1.2.6 检测方法的特异性、灵敏度和可靠性
以1.2.2中提取的6种猪(恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪)、13种其他动物(鸡、鸭、鹅、牛、驴、羊、狗、鱼、鱿鱼、虾、扇贝、骆驼、小鼠)和5种植物(大豆、小麦、玉米在食品添加剂中常见,拟南芥和烟草为模式植物)的基因组DNA为模板,按照1.2.5中反应程序与体系进行实时荧光PCR扩增,验证检测方法对猪扩增的稳定性,以及对其他动物和植物的特异性。将猪基因组DNA梯度稀释至20、4、0.8、0.16、0.032、0.0064 ng/μL,以其作为模板进行TaqMan实时荧光定量PCR扩增,考察检测方法的灵敏度和可靠性。
1.2.7 样品检测
将20 ng/µL的猪DNA与20 ng/µL的羊DNA混合,制成猪DNA含量分别50%、20%、10%、1%、0.1%、0%的DNA混合样品,以之为模板进行荧光定量PCR检测。将猪肉粉末与羊肉粉末混合,猪肉粉末含量分别为50%、20%、10%、5%、1%、 0%,将混合的肉样品提取基因组DNA后,进行荧光定量PCR检测。
1.3 数据处理
实验设置3个平行,每组实验重复3次,结果以3次重复的平均值±标准偏差(SD)表示。利用CFX96定量PCR仪自带的软件Bio-Rad CFX Maestro 1.0分析荧光定量PCR扩增曲线和Ct值。利用Microsoft Excel 2016对实验数据进行统计分析。
2. 结果与分析
2.1 候选DNA序列的筛选
通过对猪的全基因组序列的自我比对以及Blastn分析,筛选到猪细胞核基因组中的单拷贝基因(XM021097549,carcinoembryonic antigen-related cell adhesion molecule 2-like,CACA)。以之为模板设计多对引物序列,利用SYBR Green Ⅰ实时荧光定量PCR对不同引物对进行比较,选取扩增曲线稳定、熔解峰清晰单一的引物对,并设计Taq-man探针。最终选取的引物探针序列如表2所示,该序列的Blastn分析结果如图1所示,比对结果表明该序列在其他生物中均无相似性高的序列。
2.2 物种特异性鉴定
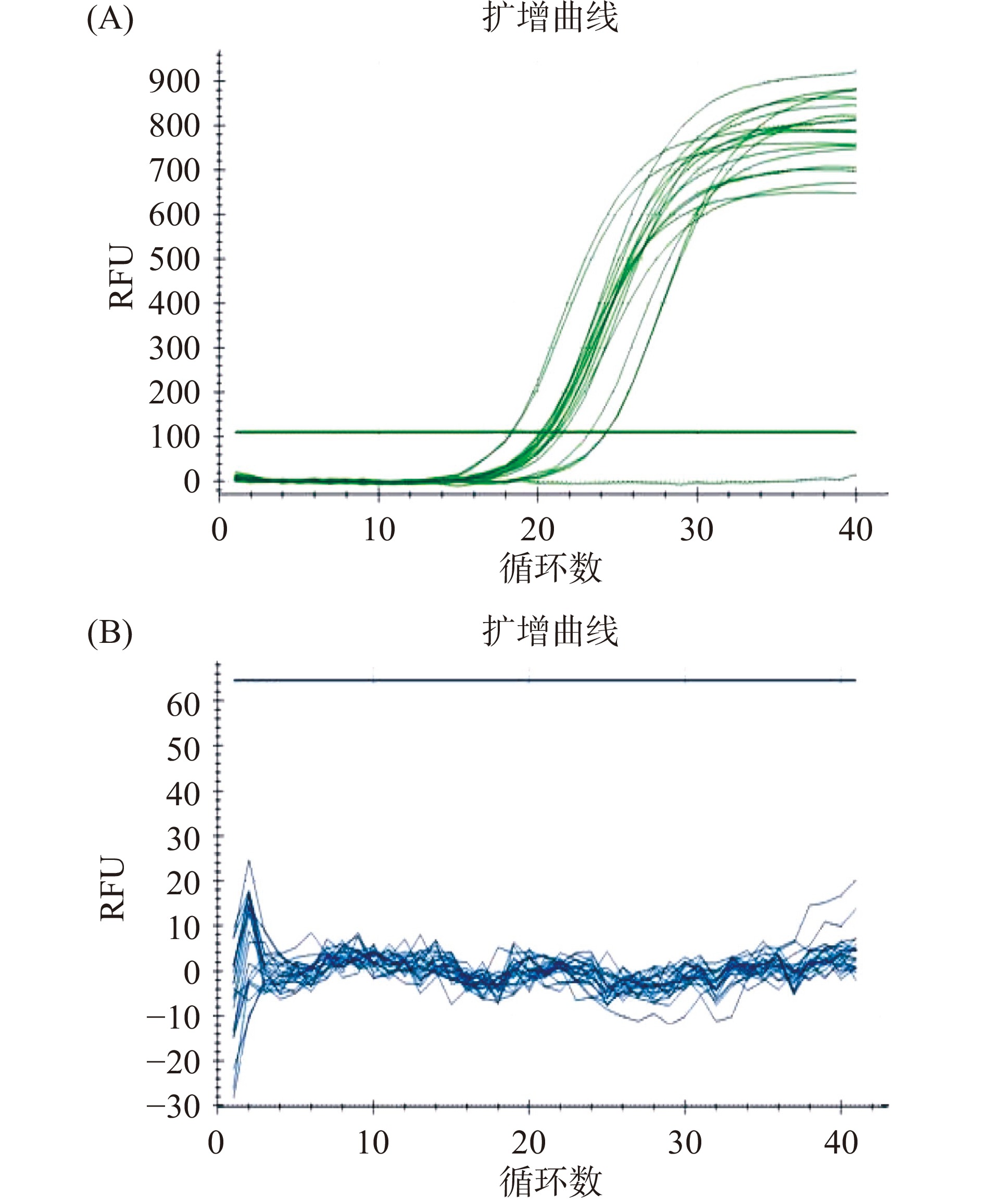
以13种其他动物(鸡、鸭、鹅、牛、驴、羊、狗、鱼、鱿鱼、虾、扇贝、骆驼、小鼠)和5种植物(大豆、小麦、玉米在食品添加剂中常见,拟南芥和烟草为模式植物)的基因组DNA为模板,进行种外扩增特异性实验。首先利用18S rDNA基因引物对上述18份基因组DNA进行SYBR Green I实时荧光定量PCR扩增,结果均有典型的扩增曲线,空白对照无扩增,表明DNA具有良好的可扩增性(图2A)。以引物探针组合CACAF21/R162/P69对上述18份基因组DNA进行种外扩增特异性实验。结果显示该引物探针组合对13种其他动物以及5种植物的基因组DNA均无扩增(图2B),表明引物探针组合CACAF21/R162/P69对其他动物和植物具有良好的特异性。
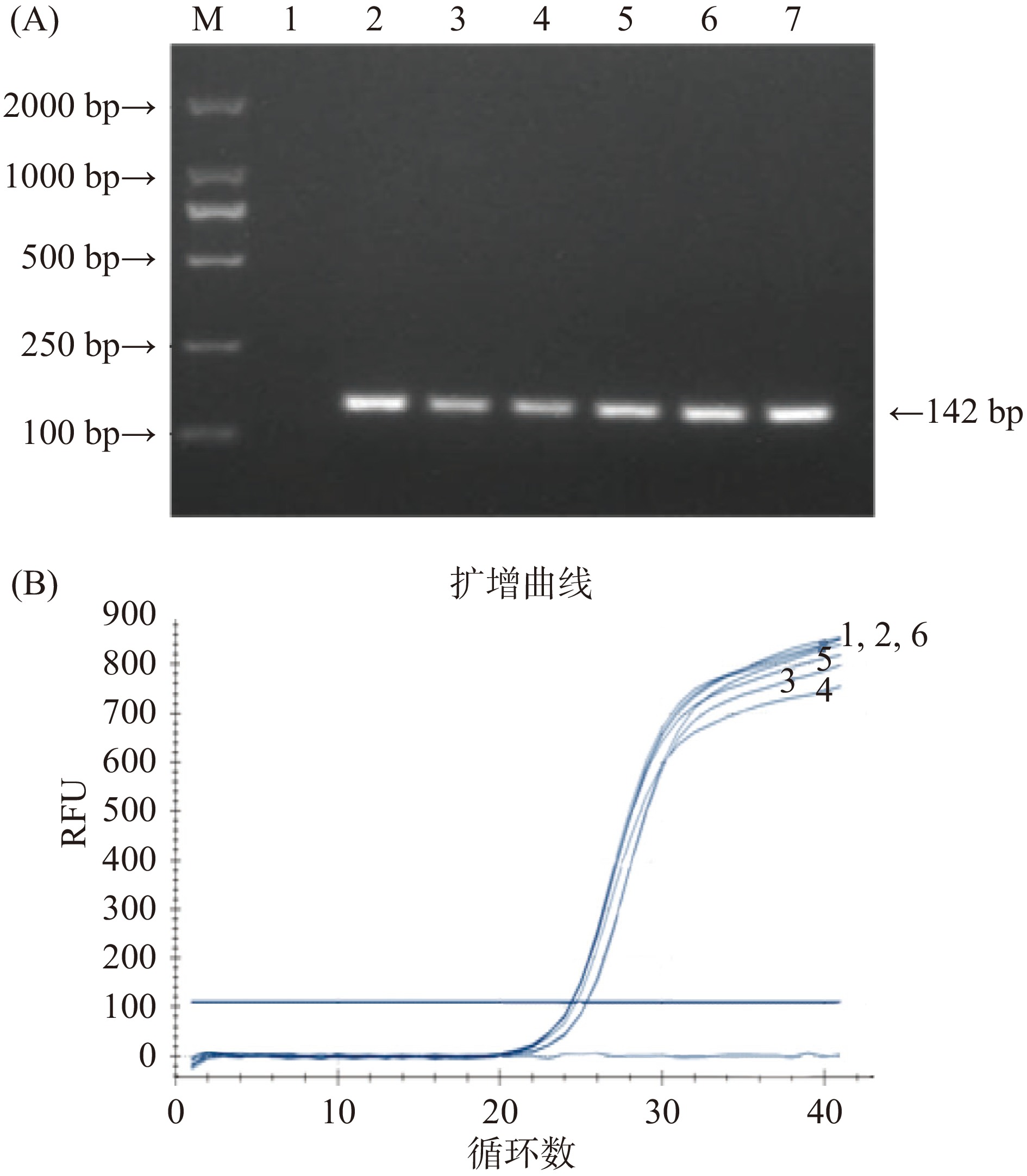
以6种猪(恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪)的基因组DNA为模板,以引物组合CACAF21/R162进行定性PCR扩增,结果均有142 bp扩增条带(图3A)。对6个扩增条带进行序列测定,DNA序列与理论上一致。以引物探针组合CACAF21/R162/P69进行TaqMan实时荧光定量PCR,均有典型的扩增曲线(图3B)。表明引物探针组合CACAF21/R162/P69在不同品种猪中一致性、稳定性好,且对其他动物和植物具有良好的特异性,可作为猪特异性的细胞核单拷贝基因用于猪源性成分的检测。
![]() 图 3 检测方法种内稳定性分析注:A: 引物组合CACAF21/ R162对6种猪的定性PCR扩增结果: M为DL2000 DNA ladder;1为空白对照;2~7分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的定性PCR扩增结果; B: 引物探针组合CACAF21/R162/P69对6种猪的定量PCR扩增结果: 1~6分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的TaqMan实时荧光定量PCR扩增曲线。Figure 3. Intra-species stability analysis of detection method
图 3 检测方法种内稳定性分析注:A: 引物组合CACAF21/ R162对6种猪的定性PCR扩增结果: M为DL2000 DNA ladder;1为空白对照;2~7分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的定性PCR扩增结果; B: 引物探针组合CACAF21/R162/P69对6种猪的定量PCR扩增结果: 1~6分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的TaqMan实时荧光定量PCR扩增曲线。Figure 3. Intra-species stability analysis of detection method2.3 检测方法的灵敏度和可靠性
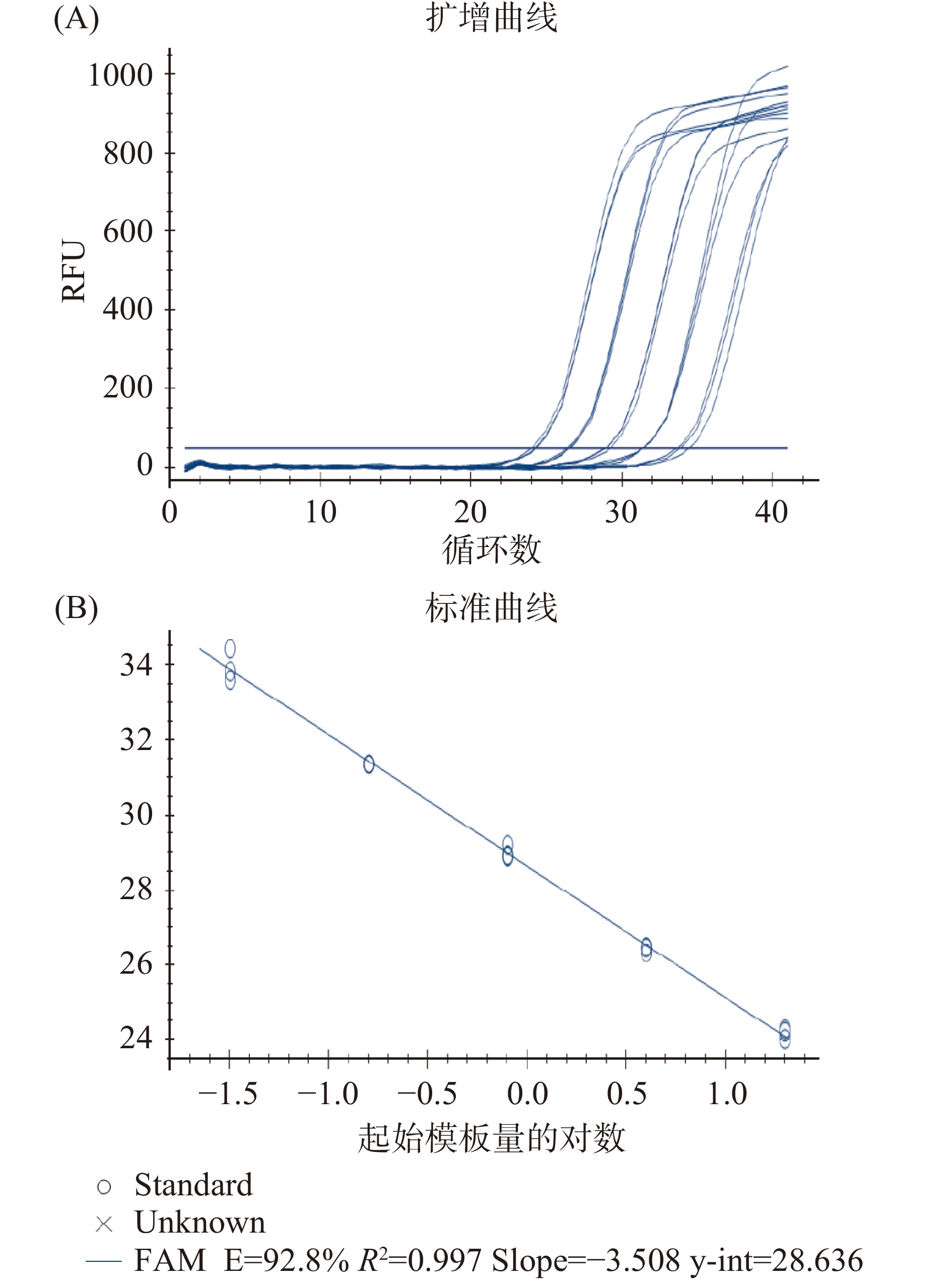
以梯度稀释的猪DNA为模板,利用CACAF21/R162/P69引物探针组合进行TaqMan实时荧光定量PCR扩增,扩增Ct值如表3所示。可检测到的模板DNA浓度低至0.032 ng/µL,表明该方法灵敏度良好。获得的扩增曲线如图4A所示,根据梯度稀释的扩增曲线可绘制标准曲线(图4B)。在20~0.032 ng/µL的DNA浓度范围内,模板DNA和扩增Ct值之间存在良好的线性关系,标准曲线为y=−3.508x+28.636,线性决定系数R2为0.997,扩增效率为92.8%,表明该方法可以用于定量检测中[23]。
表 3 猪实时荧光定量PCR方法的灵敏度和可靠性Table 3. Sensitivity and reliability of real-time quantitative PCR for detection of pig DNADNA浓度(ng/µL) Ct值 平均值 标准偏差SD 1 2 3 20 24.21 24.01 24.27 24.16 0.14 4 26.48 26.31 26.45 26.41 0.09 0.8 28.88 29.19 28.92 29.00 0.17 0.16 31.36 31.35 31.35 31.35 0.01 0.032 33.60 34.43 33.83 33.95 0.43 0.0064 36.14 36.28 / / / 2.4 模拟样品的定量检测
利用CACAF21/R162/P69引物探针组合对猪DNA含量分别50%、20%、10%、1%、0.1%、0%的DNA混合样品进行荧光定量PCR检测,模板DNA浓度为20 ng/µL,将获得的Ct值代入标准曲线,计算猪DNA的百分含量(表4)。实验结果表明,当猪DNA含量低至0.1%时,相对标准偏差为22.28%,相对误差为11.37%。
表 4 已知掺假比例的模拟混合样品的实时荧光定量PCR检测Table 4. Real-time PCR quantitative analysis of simulated samples with known adulteration ratio样品类型 理论值
(%)Ct值 平均值 标准偏差
(SD)猪DNA含量(%) 平均值(%) 标准偏差
(SD)相对标准偏差
(RSD,%)相对误差
(R.E,%)1 2 3 1 2 3 DNA
模拟样品50 25.11 25.22 25.16 25.16 0.06 50.59 47.07 48.96 48.88 1.76 3.61 -2.25 20 26.48 26.33 26.44 26.42 0.08 20.59 22.72 21.13 21.48 1.11 5.15 7.39 10 27.34 27.41 27.72 27.49 0.20 11.71 11.18 9.12 10.67 1.37 12.80 6.70 1 31.07 30.73 31.06 30.95 0.19 1.01 1.26 1.02 1.10 0.14 13.13 9.85 0.1 34.76 34.51 34.10 34.46 0.33 0.09 0.11 0.14 0.11 0.02 22.28 11.37 0 / / / / / / / / / / / / 肉
模拟样品50 25.13 25.15 25.53 25.27 0.23 49.94 49.28 38.40 45.87 6.48 14.12 -8.25 20 26.30 26.36 26.55 26.40 0.13 23.17 22.27 19.66 21.70 1.82 8.40 8.50 10 27.27 27.60 27.45 27.44 0.17 12.26 9.87 10.89 11.01 1.20 10.88 10.06 5 28.23 28.50 28.70 28.48 0.24 6.53 5.47 4.79 5.60 0.87 15.61 11.92 1 31.06 31.19 30.50 30.92 0.37 1.02 0.94 1.47 1.14 0.29 25.25 14.16 0 / / / / / / / / / / / / 对猪肉粉末含量分别为50%、20%、10%、5%、1%、0%的肉样品提取基因组DNA后,进行荧光定量PCR检测,将获得的Ct值代入标准曲线,计算猪DNA的百分含量(表4)。实验结果表明,当肉粉中猪肉含量为5%时,相对标准偏差为15.61%,相对误差为11.92%,当肉粉中猪肉含量为1%时,相对标准偏差为25.25%,相对误差为14.16%。根据CAC/GL 74-2010对基于DNA的定量检测方法的要求,RSD值应不超过25%。因此该方法可以检测DNA含量低至0.1%的混合DNA样品,以及肉含量低至5%的混合肉制品。
2.5 市售肉制品的检测
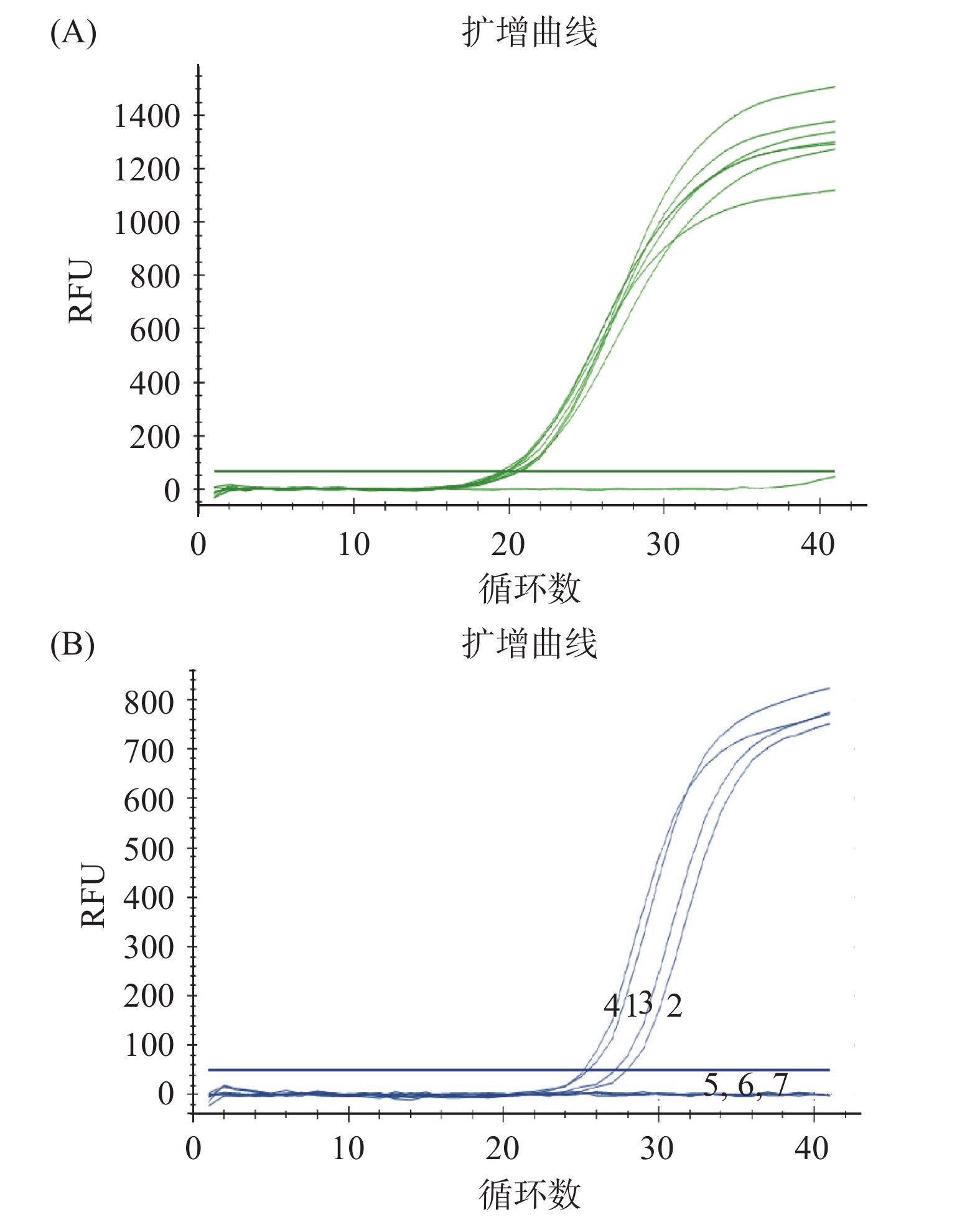
将所建立的实时荧光定量检测方法对菜场牛肉丸、鱼丸、超市品牌牛肉丸、品牌羊肉卷、品牌肥羊卷、品牌肥牛卷、品牌牛排等7种市售肉制品进行检测,同时以
18S rDNA的扩增证明DNA的可扩增性。检测结果如图5和表5所示。菜场的牛肉丸、鱼丸、超市品牌牛肉丸、品牌羊肉卷基因组DNA均对CACAF21/R162/P69引物探针组合有典型的扩增,证明其中含有猪肉成分。将获得的Ct值代入标准曲线,按20 ng/µL的总DNA计算,其中猪肉DNA 含量分别为41.83%、8.03%、13.32%、49.39%,表明在菜场牛肉和超市品牌羊肉卷中含有较多的猪肉成分。菜场的牛肉丸、鱼丸标签上均未标识含有猪肉成分,因此在市场上确实存在欺瞒消费者的情况。超市品牌牛肉丸和品牌羊肉卷在其配料表中注明含有猪肉成分,但是并未标识出含量,通过检测发现品牌羊肉卷中含有大量的猪肉。通过市售肉制品的检测,表明本研究建立的方法可以准确可靠地判定肉制品中是否含有猪肉成分,并可用于猪肉成分的定量检测。 表 5 市售肉制品的实时荧光定量PCR检测Table 5. Real-time PCR quantitative analysis of commercial available meat products编号 样品名称 CACA Ct值 平均值 标准偏差
(SD)猪DNA含量(%) 平均值(%) 标准偏差
(SD)相对标准偏差
(RSD,%)1 2 3 1 2 3 1 菜场牛肉丸 25.38 25.37 25.45 25.40 0.04 42.38 42.66 40.47 41.83 1.19 2.84 2 菜场鱼丸 28.00 27.97 27.77 27.91 0.13 7.59 7.74 8.83 8.03 0.67 8.40 3 超市品牌牛肉丸 27.11 27.10 27.22 27.14 0.07 13.61 13.70 12.67 13.32 0.58 4.32 4 超市品牌羊肉卷 25.21 25.02 25.21 25.15 0.11 47.38 53.67 47.38 49.39 3.63 7.36 5 超市品牌肥羊卷 / / / / / / / / / / / 6 超市品牌肥牛卷 / / / / / / / / / / / 7 超市品牌牛排 / / / / / / / / / / / 3. 结论与讨论
肉制品掺假事件屡屡发生,建立有效的检测方法对维护消费者权益,保障肉制品贸易公平性具有重要意义[24]。细胞核基因较线粒体基因具有更强的定量准确性[25-26],近年来越来越多的研究利用细胞核单拷贝基因对动物源物种成分进行定量检测。WU等[27]建立了基于细胞核单拷贝基因的实时荧光定量PCR方法,对狐狸、貂、狗、兔进行特异性检测,可对掺杂含量低至5%的DNA样品准确检测。唐廷廷[28]以山羊CAST基因、鸡CAPN2基因为靶标,建立了能实现定量检测羊肉中鸡肉质量百分比的方法,最低检测极限可达5%(w/w)。CAI等[29]以鸡TGFB3基因、猪β-actin基因为靶标,建立数字PCR方法对肉制品中鸡肉和猪肉含量进行定量检测,可准确检测含量低至10%(w/w)的鸡肉和猪肉成分。值得注意的是,由于不同动物、不同组织、同一动物不同组织单位重量样品的DNA含量不同,DNA提取效率也不尽相同,动物DNA拷贝数与组织重量间没有明确的换算关系,因此,在检测加工肉制品时,难以通过DNA拷贝数百分比来直接计算样品中某一种肉组分的含量[30]。
本研究以猪特异的细胞核单拷贝基因为研究对象,通过生物信息学方法筛选到猪细胞核单拷贝基因CACA,并建立了基于猪CACA基因的Taq-man实时荧光定量PCR检测方法。研究结果表明,该方法特异性强、灵敏度高,在20~0.032 ng/µL的DNA浓度范围内,模板DNA和扩增Ct值之间存在良好的线性关系。在相对标准偏差≤25%的条件下,可准确检测猪DNA含量低至0.1%的DNA样品,猪肉含量低至5.0%(w/w)的肉制品。该方法的灵敏度和准确性与其他基于细胞核基因的检测方法相当[26-31]。对市售的肉制品检测结果表明,目前市场上存在含有猪肉成分却未标识,以及标识有猪肉成分但含量无法得知的情况。本研究建立的方法可准确识别出肉制品中是否含有猪肉成分,并可用于猪肉含量的定量检测,可为肉制品日常检测及是否掺假提供有力的科学依据。
-
图 3 检测方法种内稳定性分析
注:A: 引物组合CACAF21/ R162对6种猪的定性PCR扩增结果: M为DL2000 DNA ladder;1为空白对照;2~7分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的定性PCR扩增结果; B: 引物探针组合CACAF21/R162/P69对6种猪的定量PCR扩增结果: 1~6分别为以恩施黑猪、恩施土猪、黄陂土猪、双汇猪肉、中粮猪肉、野猪基因组DNA为模板的TaqMan实时荧光定量PCR扩增曲线。
Figure 3. Intra-species stability analysis of detection method
表 1 特异性验证实验中所用到的材料的详细信息
Table 1 Detailed information about the materials used in species specificity analysis
样品编号 种类 通用名 学名 1 家禽 鸡 Gallus gallus 2 鸭 Anas platyrhynchos 3 鹅 Anser domestica 4 家畜 牛 Bos taurus 5 驴 Equus asinus 6 绵羊 Ovis aries 7 猪 Sus scrofa 8 狗 Canis lupus familiaris 9 水产品 草鱼 Ctenopharyngodon idella 10 鱿鱼 Illex argentines 11 虾 Penaeus orientalis 12 扇贝 Patinopecten yessoensis 13 模式动物 小鼠 Mus musculus 14 其他动物 骆驼 Camelus bactrianus 15 植物 大豆 Glycine max 16 小麦 Triticum aestivum 17 玉米 Zea mays 18 拟南芥 Arabidopsis thaliana 19 烟草 Nicotiana tabacum 表 2 引物和探针的序列
Table 2 Primer and probe sequences
引物和探针 序列(5’-3’) 靶基因 18S-EUKF AGCCTGCGGCTTAATTTGAC 18S rDNA 18S-EUKR CAACTAAGAACGGCCATGCA CACAF21 CAGCCACTTCCCAGGATACC CACA CACAR162 CCACTGTCCAACACTCGCAC CACAP69 FAM-ACGCCCTCACTCCAGAACCAGCC-BHQ1 表 3 猪实时荧光定量PCR方法的灵敏度和可靠性
Table 3 Sensitivity and reliability of real-time quantitative PCR for detection of pig DNA
DNA浓度(ng/µL) Ct值 平均值 标准偏差SD 1 2 3 20 24.21 24.01 24.27 24.16 0.14 4 26.48 26.31 26.45 26.41 0.09 0.8 28.88 29.19 28.92 29.00 0.17 0.16 31.36 31.35 31.35 31.35 0.01 0.032 33.60 34.43 33.83 33.95 0.43 0.0064 36.14 36.28 / / / 表 4 已知掺假比例的模拟混合样品的实时荧光定量PCR检测
Table 4 Real-time PCR quantitative analysis of simulated samples with known adulteration ratio
样品类型 理论值
(%)Ct值 平均值 标准偏差
(SD)猪DNA含量(%) 平均值(%) 标准偏差
(SD)相对标准偏差
(RSD,%)相对误差
(R.E,%)1 2 3 1 2 3 DNA
模拟样品50 25.11 25.22 25.16 25.16 0.06 50.59 47.07 48.96 48.88 1.76 3.61 -2.25 20 26.48 26.33 26.44 26.42 0.08 20.59 22.72 21.13 21.48 1.11 5.15 7.39 10 27.34 27.41 27.72 27.49 0.20 11.71 11.18 9.12 10.67 1.37 12.80 6.70 1 31.07 30.73 31.06 30.95 0.19 1.01 1.26 1.02 1.10 0.14 13.13 9.85 0.1 34.76 34.51 34.10 34.46 0.33 0.09 0.11 0.14 0.11 0.02 22.28 11.37 0 / / / / / / / / / / / / 肉
模拟样品50 25.13 25.15 25.53 25.27 0.23 49.94 49.28 38.40 45.87 6.48 14.12 -8.25 20 26.30 26.36 26.55 26.40 0.13 23.17 22.27 19.66 21.70 1.82 8.40 8.50 10 27.27 27.60 27.45 27.44 0.17 12.26 9.87 10.89 11.01 1.20 10.88 10.06 5 28.23 28.50 28.70 28.48 0.24 6.53 5.47 4.79 5.60 0.87 15.61 11.92 1 31.06 31.19 30.50 30.92 0.37 1.02 0.94 1.47 1.14 0.29 25.25 14.16 0 / / / / / / / / / / / / 表 5 市售肉制品的实时荧光定量PCR检测
Table 5 Real-time PCR quantitative analysis of commercial available meat products
编号 样品名称 CACA Ct值 平均值 标准偏差
(SD)猪DNA含量(%) 平均值(%) 标准偏差
(SD)相对标准偏差
(RSD,%)1 2 3 1 2 3 1 菜场牛肉丸 25.38 25.37 25.45 25.40 0.04 42.38 42.66 40.47 41.83 1.19 2.84 2 菜场鱼丸 28.00 27.97 27.77 27.91 0.13 7.59 7.74 8.83 8.03 0.67 8.40 3 超市品牌牛肉丸 27.11 27.10 27.22 27.14 0.07 13.61 13.70 12.67 13.32 0.58 4.32 4 超市品牌羊肉卷 25.21 25.02 25.21 25.15 0.11 47.38 53.67 47.38 49.39 3.63 7.36 5 超市品牌肥羊卷 / / / / / / / / / / / 6 超市品牌肥牛卷 / / / / / / / / / / / 7 超市品牌牛排 / / / / / / / / / / / -
[1] ABBOTS E J, COLES B. Horsemeat-gate: The discursive production of a neoliberal food scandal[J]. Food Culture & Society an International Journal of Multidisciplinary Research,2013,16(4):535−550.
[2] 高敬, 魏迪, 张癸荣, 等. 常见肉类鉴别技术研究进展[J]. 食品科学,2014,35(11):356−360. [GAO J, WEI D, ZHANG G R, et al. Recent progress on commonly used techniques for identification of meat species[J]. Food Science,2014,35(11):356−360. doi: 10.7506/spkx1002-6630-201411068 [3] BARNARD C, O'CONNOR N. Runners and riders: The horsemeat scandal, eu law and multi-level enforcement[J]. The Cambridge Law Journal,2017,76(1):116−144. doi: 10.1017/S000819731700006X
[4] 张玉华, 孟一, 姜沛宏, 等. 近红外技术对不同动物来源肉掺假的检测[J]. 食品工业科技,2015,36(3):316−319,334. [ZHANG Y H, MENG Y, JIANG P H, et al. Detection of adulteration of animal meats from different sources by near infrared technology[J]. Science and Technology of Food Industry,2015,36(3):316−319,334. [5] QAMAR Z, MOHAMMAD A, KHAIRIL M N F, et al. Current analytical methods for porcine identification in meat and meat products[J]. Food Chemistry,2020,324(1):126664−126693.
[6] 任君安, 黄文胜, 葛毅强, 等. 肉制品真伪鉴别技术研究进展[J]. 食品科学,2016,37(1):247−257. [REN J A, HUANG W S, GE Y Q, et al. Progress in meat adulteration detection techniques[J]. Food Science,2016,37(1):247−257. doi: 10.7506/spkx1002-6630-201601043 [7] BALLIN N Z. Authentication of meat and meat products[J]. Meat Science,2010,86(3):577−587. doi: 10.1016/j.meatsci.2010.06.001
[8] 中国标准化研究院, 四川华汉三创生物科技有限公司, 山东省食品药品检验研究院, 等. GB/T 35917-2018常见动物源性成分快速测定 膜芯片法[S]. 北京: 中华人民共和国国家质量监督检验检疫总局, 中国国家标准化管理委员会, 2018. CNIS, Sichuan Huahan Trio Biotech, Shandong Institute for Food and Drug Control, et al. GB/T 35917-2018 Rapid detection for animal-derived materials—membrane-based array method[S]. Beijing: General Administration of Quality Supervision, Inspection and Quarantine of the People's Republic of China, Standardization Administration of the People’s Republic of China, 2018.
[9] CAMMA C, DI DOMENICO M, MONACO F. Development and validation of fast real-time PCR assays for species identification in raw and cooked meat mixtures[J]. Food Control,2012,23(2):400−404. doi: 10.1016/j.foodcont.2011.08.007
[10] SAFDAR M, JUNEJO Y. Development and validation of fast duplex real-time PCR assays based on SYBER Green florescence for detection of bovine and poultry origins in feedstuffs[J]. Food Chemistry,2015,173:660−664. doi: 10.1016/j.foodchem.2014.10.088
[11] KIM M, YOO I, LEE S Y, et al. Quantitative detection of pork in commercial meat products by Taqman(r) real-time PCR assay targeting the mitochondrial D-loop region[J]. Food Chemistry,2016,210:102−106. doi: 10.1016/j.foodchem.2016.04.084
[12] HAIDER N, NABULSI I, AL-SAFADI B. Identification of meat species by PCR-RFLP of the mitochondrial COI gene[J]. Meat Science,2012,90(2):490−493. doi: 10.1016/j.meatsci.2011.09.013
[13] AMARAL J S, SANTOS C G, MELO V S, et al. Identification of duck, partridge, pheasant, quail, chicken and turkey meats by species-specific PCR assays to assess the authenticity of traditional game meat alheira sausages[J]. Food Control,2015,47:190−195. doi: 10.1016/j.foodcont.2014.07.009
[14] 王婷. 鸡线粒体DNA拷贝数差异研究[D]. 郑州: 河南农业大学, 2017. WANG T. Study on the variation of mitochondrial DNA copy number in chicken[D]. Zhengzhou: Henan Agricultural University, 2017.
[15] 彭媛媛, 武煊, 陶晓奇. 实时荧光PCR技术定量检测肉类掺假的研究进展[J]. 食品与发酵工业,2019,45(15):279−287. [PENG Y Y, WU X, TAO X Q. Quantitative detection of meat adulteration by real-time fluorescent PCR[J]. Food and Fermentation Industries,2019,45(15):279−287. [16] BALLIN N Z, VOGENSEN F K, KARLSSON A H. Species determination–can we detect and quantify meat adulteration?[J]. Meat Science,2009,83(2):165−174. doi: 10.1016/j.meatsci.2009.06.003
[17] 纪艺, 徐晓丽, 姜媛媛, 等. 基于数字PCR的不同品种鸭组织中线粒体与核DNA拷贝数差异研究[J]. 生物技术通报,2020,36(5):86−91. [JI Y, XU X L, JIANG Y Y, et al. Copy number variations of mitochondrial DNA and genomic DNA from different tissues of duck based on digital PCR[J]. Biotechnology Bulletin,2020,36(5):86−91. [18] FLOREN C, WIEDEMANN I, BRENIG B, et al. Species identification and quantification in meat and meat products using droplet digital PCR (ddpcr)[J]. Food Chemistry,2015,173:1054−1058. doi: 10.1016/j.foodchem.2014.10.138
[19] 陈晨, 张岩, 李永波, 等. 微滴式数字PCR对肉制品中羊肉和猪肉定量分析[J]. 现代食品科技,2018,34(1):221−226,194. [CHEN C, ZHANG Y, LI Y B, et al. Quantitative analysis of mutton and pork in meat products by micro digital PCR[J]. Modern Food Science and Technology,2018,34(1):221−226,194. [20] 支琴, 郭金超, 龚强. 肉制品中动物源性成分DNA检测方法的研究进展[J]. 食品安全质量检测学报,2018,9(16):4204−4211. [ZHI Q, GUO J C, GONG Q. Advance in DNA analytical techniques for ingredients of animal origin in meat products[J]. Journal of Food Safety & Quality,2018,9(16):4204−4211. doi: 10.3969/j.issn.2095-0381.2018.16.004 [21] 汪永庆, 王新国, 徐来祥, 等. 一种动物基因组DNA提取方法的改进[J]. 动物学杂志,2001,36(1):27−29. [WANG Y Q, WANG X G, XU L X, et al. A new rapid method for extraction of high quality of genomic DNA from animal tissues[J]. Chinese Journal of Zoology,2001,36(1):27−29. doi: 10.3969/j.issn.0250-3263.2001.01.007 [22] LOPEZ-ANDREO M, LUGO L, GARRIDO-PERTIERRA A, et al. Identification and quantitation of species in complex DNA mixtures by real-time polymerase chain reaction[J]. Anal Biochem,2005,339(1):73−82. doi: 10.1016/j.ab.2004.11.045
[23] FAO, WHO. CAC/GL 74-2010 guidelines on performance criteria and validation of methods for detection, identification and quantification of specific DNA sequences and specific proteins in foods[S]. Codex Alimentarius, 2010.
[24] REN J, DENG T, HUANG W, et al. A digital PCR method for identifying and quantifying adulteration of meat species in raw and processed food[J]. Plos One,2017,12(3):e0173567. doi: 10.1371/journal.pone.0173567
[25] WANG W, FU M, ZHANG Q, et al. A novel quantitative real-time PCR method for the detection of mammalian and poultry species based on a shared single-copy nuclear DNA sequence[J]. Food Chemistry,2021,341(2):128170−128179.
[26] 张秀平, 苗丽. 实时荧光PCR定量测定肉制品中羊源性成分[J]. 食品工业科技,2019,40(7):119−123,130. [ZHANG X P, MIAO L. Quantitative detection of ovine-derived materials in meat products by real-time fluorescent PCR[J]. Science and Technology of Food Industry,2019,40(7):119−123,130. [27] WU Q, XIANG S, WANG W, et al. Species identification of fox-, mink-, dog-, and rabbit-derived ingredients by multiplex PCR and real-time PCR assay[J]. Applied Biochemistry and Biotechnology,2018,185(1):1−12. doi: 10.1007/s12010-017-2621-2
[28] 唐廷廷. 羊肉中鸡源性成分实时荧光定量PCR量化检测技术研究[D]. 雅安: 四川农业大学, 2018. TANG T T. Quantitative detection of chicken-derived components in mutton by real-time quantitative PCR[D]. Yaan: Sichuan Agricultural University, 2018.
[29] CAI Y C, LI X, LV R, et al. Quantitative analysis of pork and chicken products by droplet digital PCR[J]. Biomed Research International,2014,2014:810209−810214.
[30] 张艳, 井汇源, 孙彦婷, 等. 数字PCR精准定量方法研究进展[J]. 中国草食动物科学,2020,40(6):55−59,80. [ZHANG Y, JING H Y, SUN Y T, et al. Research progress on precise quantitative methods of digital PCR[J]. China Herbivore Science,2020,40(6):55−59,80. doi: 10.3969/j.issn.2095-3887.2020.06.013 [31] 李婷婷. 基于DNA检测的羊肉掺假鉴别技术研究[D]. 北京: 中国农业科学院, 2019. LI T T. Development of DNA-base identification technologies for mutton adulteration[D]. Beijing: Chinese Academy of Agricultural Sciences, 2019.
-
期刊类型引用(26)
1. 王红,彭励,宋乐,冯璐,李振凯,李彦青,高跳. 银柴胡多糖超声辅助提取工艺优化及抗氧化活性分析. 食品工业科技. 2024(01): 185-191 .  本站查看
本站查看
2. 赵小亮,鲁雲,康兴兴,龙则宇,郑晓杰. 雁荡山铁皮石斛多糖的提取、结构表征与体外抗氧化活性. 浙江农业学报. 2024(08): 1898-1908 .  百度学术
百度学术
3. 刘丽宅,张鑫,金香淑,王蕾,赵云辉,王多伽,刘笑笑. 响应面法优化猪肉TPA质构测试条件. 东北农业科学. 2024(05): 100-108 .  百度学术
百度学术
4. 张艳,刘雪松,薛沾枚,冯万宇,张备,张蕾,沈思思,武晓东,张国华,江波涛. 麻杏石甘汤处方药材研究进展. 现代畜牧科技. 2023(01): 5-8 .  百度学术
百度学术
5. 刘宇,戴沅霖,马越,董淑君,张斌,郑振佳. 金银花粗多糖提取工艺优化及其抗氧化活性评价. 食品工业科技. 2023(07): 188-196 .  本站查看
本站查看
6. 王珏,张华,王丹,唐宇,常兵. 乳化液膜法处理石油石化废水的研究. 油气田环境保护. 2023(02): 6-12 .  百度学术
百度学术
7. 曹建蕾. 响应面法优化枸杞多糖的超声辅助提取工艺. 安徽化工. 2023(03): 105-109+113 .  百度学术
百度学术
8. 徐瑾钰,彭小伟,阚欢,赵平,全伟,刘云. 滇皂角米多糖提取工艺优化及其抗氧化活性. 食品研究与开发. 2023(14): 112-118 .  百度学术
百度学术
9. 邹湘月,李章保,李霞,叶添梅,邵元元,米雅兰,艾均文,李飞鸣. 90份桑树种质资源桑叶品质的综合评价. 蚕业科学. 2023(04): 313-323 .  百度学术
百度学术
10. 董巍,王文豹,王晓丽,付双,野津. 超声法辅助提取内蒙古甘草多糖工艺及其抗氧化活性研究. 现代食品. 2023(16): 91-95 .  百度学术
百度学术
11. 高昆,林洪源. 山西省道地中药材研究进展. 山西农业科学. 2023(12): 1457-1467 .  百度学术
百度学术
12. 杨奕凡,高雁,刘亚男,霍向东,娄恺,关波,陈开旭,曾军. 甘草渣中活性成分的提取及其在动物生产中的应用. 饲料研究. 2023(23): 140-143 .  百度学术
百度学术
13. 余捷,李亚娜,夏瑾瑾,闫普普,刘佳丽,郭利伟,杨小林,刘国平,易提林. 复合酶辅助提取荷叶多糖工艺优化及其体外抗氧化活性. 食品研究与开发. 2023(24): 115-121 .  百度学术
百度学术
14. 杨元华,范馨予,高红艳. 响应面法优化白番红花球茎多糖提取工艺及其抗氧化活性研究. 伊犁师范大学学报(自然科学版). 2023(04): 36-47 .  百度学术
百度学术
15. 刘玉洁,董丽婷,罗灿,陈劭舒,夏凤腾,王征. 枯草芽孢杆菌LY-05发酵玉竹产水溶性多糖工艺优化及其抗氧化活性研究. 食品工业科技. 2022(03): 212-221 .  本站查看
本站查看
16. 张艳,孟维珊,陈曦,刘雪松,薛沾枚,王爽,杨旭东,朱庆贺,罗天瑶,张备,黄红,徐婷婷,史同瑞. 中兽药处方桂枝汤药材研究进展. 现代畜牧科技. 2022(05): 17-20 .  百度学术
百度学术
17. 姚月华,唐宁,应熙锐,应朝阳,程永强. 红萍多糖结构特征、流变特性及抗氧化活性. 食品与机械. 2022(03): 154-159+172 .  百度学术
百度学术
18. 张艳,刘雪松,薛沾枚,张备,尹珺伊,张军,王岩,张蕾,沈思思,史同瑞. 兽用理中汤处方药材研究进展. 中国草食动物科学. 2022(03): 51-54 .  百度学术
百度学术
19. 李幼娟,李立郎,陈发菊,王丽,葛丽娟,文平,国光梅,杨小生. 天麻酒渗漉工艺优化及其对小鼠肝组织的影响. 中国酿造. 2022(07): 116-121 .  百度学术
百度学术
20. 则拉莱·司玛依,帕尔哈提·柔孜,吾哈丽妮萨·麦麦提托合提,古丽米热·阿巴拜克日,邓杰,杨晓君. 三种甘草种子蛋白的提取方法、结构及抗氧化活性比较研究. 食品与发酵工业. 2022(18): 227-234 .  百度学术
百度学术
21. 陈文彬,王雪莹,张才,马彦博,程源斌,王国永,孔涛,廖成水. 甘草多糖对肉鸡生长性能和免疫功能的影响. 饲料研究. 2022(18): 34-40 .  百度学术
百度学术
22. 赵泽林,张丽艳,晋海军,李军,唐晓琴,董贺,周芳丽,马四补. 响应面法优化油炙淫羊藿炮制工艺及抗氧化活性分析. 亚太传统医药. 2022(12): 76-80 .  百度学术
百度学术
23. 罗灿,刘玉洁,陈劭舒,夏凤腾,李怡成,王征. 灵芝菌液体发酵玉竹产水溶性多糖的工艺优化和抗氧化性研究. 中国酿造. 2022(11): 180-186 .  百度学术
百度学术
24. 董贺,李军,晋海军,唐晓琴,赵泽林,孙恒灿,张丽艳. 响应面法优化大蝎子草水溶性总黄酮提取工艺及其水提液抗氧化活性分析. 贵州科学. 2022(06): 31-36 .  百度学术
百度学术
25. 朱玉婷,文欣,向俊,郭锦材,荆辉华,李灿,陈同强. 植物乳杆菌胞外多糖的单糖组成及抗氧化活性. 乳业科学与技术. 2022(06): 7-11 .  百度学术
百度学术
26. 宋玲玲,王君明,弓明珠,张月月,张振凌,王彦嵋,巫晓慧,郭旭. 炮制对雷公藤诱导的睾丸生殖毒性的减毒作用机制研究. 时珍国医国药. 2021(11): 2664-2667 .  百度学术
百度学术
其他类型引用(5)





 下载:
下载:

 下载:
下载:
